This pipeline computes the correlation between significantly recurrent gene mutations and selected clinical features.
Testing the association between mutation status of 158 genes and 13 clinical features across 172 patients, 9 significant findings detected with Q value < 0.25.
-
SMARCA4 mutation correlated to 'HISTOLOGICAL.TYPE'.
-
U2AF1 mutation correlated to 'HISTOLOGICAL.TYPE'.
-
MYL10 mutation correlated to 'LYMPH.NODE.METASTASIS'.
-
GBA3 mutation correlated to 'HISTOLOGICAL.TYPE'.
-
SVOP mutation correlated to 'LYMPH.NODE.METASTASIS'.
-
KRT28 mutation correlated to 'LYMPH.NODE.METASTASIS'.
-
SPATA18 mutation correlated to 'LYMPH.NODE.METASTASIS'.
-
HCK mutation correlated to 'LYMPH.NODE.METASTASIS'.
-
OR13G1 mutation correlated to 'HISTOLOGICAL.TYPE'.
Table 1. Get Full Table Overview of the association between mutation status of 158 genes and 13 clinical features. Shown in the table are P values (Q values). Thresholded by Q value < 0.25, 9 significant findings detected.
|
Clinical Features |
Time to Death |
AGE | GENDER |
KARNOFSKY PERFORMANCE SCORE |
HISTOLOGICAL TYPE |
RADIATIONS RADIATION REGIMENINDICATION |
NUMBERPACKYEARSSMOKED | YEAROFTOBACCOSMOKINGONSET |
DISTANT METASTASIS |
LYMPH NODE METASTASIS |
COMPLETENESS OF RESECTION |
TUMOR STAGECODE |
NEOPLASM DISEASESTAGE |
||
| nMutated (%) | nWild-Type | logrank test | t-test | Fisher's exact test | t-test | Chi-square test | Fisher's exact test | t-test | t-test | Fisher's exact test | Chi-square test | Fisher's exact test | t-test | Chi-square test | |
| SMARCA4 | 14 (8%) | 158 |
0.735 (1.00) |
0.775 (1.00) |
0.171 (1.00) |
5.94e-07 (0.00102) |
1 (1.00) |
0.657 (1.00) |
0.188 (1.00) |
0.509 (1.00) |
0.893 (1.00) |
1 (1.00) |
0.469 (1.00) |
||
| U2AF1 | 6 (3%) | 166 |
0.436 (1.00) |
0.894 (1.00) |
0.22 (1.00) |
1.18e-08 (2.04e-05) |
0.356 (1.00) |
0.762 (1.00) |
0.265 (1.00) |
0.0983 (1.00) |
0.277 (1.00) |
0.396 (1.00) |
0.466 (1.00) |
||
| MYL10 | 5 (3%) | 167 |
0.604 (1.00) |
0.423 (1.00) |
1 (1.00) |
0.934 (1.00) |
0.307 (1.00) |
0.221 (1.00) |
1 (1.00) |
4.04e-07 (0.000696) |
0.253 (1.00) |
0.163 (1.00) |
|||
| GBA3 | 8 (5%) | 164 |
0.357 (1.00) |
0.0276 (1.00) |
0.728 (1.00) |
1.34e-06 (0.00231) |
1 (1.00) |
0.0895 (1.00) |
0.379 (1.00) |
1 (1.00) |
0.152 (1.00) |
0.64 (1.00) |
0.25 (1.00) |
||
| SVOP | 7 (4%) | 165 |
0.866 (1.00) |
0.468 (1.00) |
0.704 (1.00) |
0.875 (1.00) |
1 (1.00) |
0.68 (1.00) |
0.338 (1.00) |
1 (1.00) |
5.04e-05 (0.0865) |
0.64 (1.00) |
0.567 (1.00) |
||
| KRT28 | 7 (4%) | 165 |
0.683 (1.00) |
0.922 (1.00) |
0.455 (1.00) |
0.000199 (0.342) |
0.0772 (1.00) |
0.071 (1.00) |
0.499 (1.00) |
0.499 (1.00) |
1.48e-05 (0.0254) |
1 (1.00) |
0.0202 (1.00) |
||
| SPATA18 | 8 (5%) | 164 |
0.609 (1.00) |
0.51 (1.00) |
0.728 (1.00) |
0.338 (1.00) |
1 (1.00) |
0.44 (1.00) |
0.596 (1.00) |
0.564 (1.00) |
4.72e-06 (0.00811) |
0.571 (1.00) |
0.0317 (1.00) |
||
| HCK | 6 (3%) | 166 |
0.219 (1.00) |
0.818 (1.00) |
0.688 (1.00) |
1 (1.00) |
1 (1.00) |
0.435 (1.00) |
0.709 (1.00) |
1.38e-05 (0.0237) |
0.49 (1.00) |
0.29 (1.00) |
|||
| OR13G1 | 9 (5%) | 163 |
0.137 (1.00) |
0.213 (1.00) |
1 (1.00) |
1.08e-05 (0.0185) |
1 (1.00) |
0.273 (1.00) |
0.879 (1.00) |
1 (1.00) |
0.336 (1.00) |
0.747 (1.00) |
0.439 (1.00) |
||
| CDKN2A | 8 (5%) | 164 |
0.371 (1.00) |
0.117 (1.00) |
0.728 (1.00) |
1 (1.00) |
1 (1.00) |
0.471 (1.00) |
0.0411 (1.00) |
0.725 (1.00) |
0.954 (1.00) |
1 (1.00) |
0.955 (1.00) |
||
| KRAS | 47 (27%) | 125 |
0.452 (1.00) |
0.955 (1.00) |
0.493 (1.00) |
0.428 (1.00) |
0.907 (1.00) |
0.183 (1.00) |
0.575 (1.00) |
0.779 (1.00) |
1 (1.00) |
0.672 (1.00) |
0.433 (1.00) |
0.583 (1.00) |
|
| TP53 | 87 (51%) | 85 |
0.635 (1.00) |
0.0626 (1.00) |
0.225 (1.00) |
0.74 (1.00) |
0.216 (1.00) |
1 (1.00) |
0.363 (1.00) |
0.396 (1.00) |
0.912 (1.00) |
0.654 (1.00) |
0.836 (1.00) |
0.947 (1.00) |
|
| EGFR | 22 (13%) | 150 |
0.0132 (1.00) |
0.149 (1.00) |
0.176 (1.00) |
0.708 (1.00) |
1 (1.00) |
0.485 (1.00) |
0.168 (1.00) |
0.581 (1.00) |
0.164 (1.00) |
0.466 (1.00) |
0.799 (1.00) |
||
| STK11 | 20 (12%) | 152 |
0.378 (1.00) |
0.6 (1.00) |
0.0941 (1.00) |
0.979 (1.00) |
0.634 (1.00) |
0.447 (1.00) |
0.403 (1.00) |
1 (1.00) |
0.889 (1.00) |
1 (1.00) |
0.451 (1.00) |
||
| KEAP1 | 32 (19%) | 140 |
0.748 (1.00) |
0.784 (1.00) |
1 (1.00) |
0.128 (1.00) |
0.244 (1.00) |
0.699 (1.00) |
0.179 (1.00) |
0.216 (1.00) |
0.235 (1.00) |
0.872 (1.00) |
1 (1.00) |
0.755 (1.00) |
|
| CRIPAK | 11 (6%) | 161 |
0.135 (1.00) |
0.29 (1.00) |
0.349 (1.00) |
0.00809 (1.00) |
1 (1.00) |
0.632 (1.00) |
0.636 (1.00) |
0.432 (1.00) |
0.967 (1.00) |
1 (1.00) |
0.461 (1.00) |
||
| RBM10 | 12 (7%) | 160 |
0.926 (1.00) |
0.176 (1.00) |
0.0676 (1.00) |
0.996 (1.00) |
1 (1.00) |
0.378 (1.00) |
0.139 (1.00) |
1 (1.00) |
0.377 (1.00) |
0.593 (1.00) |
0.711 (1.00) |
||
| NF1 | 21 (12%) | 151 |
0.43 (1.00) |
0.633 (1.00) |
0.819 (1.00) |
0.767 (1.00) |
0.167 (1.00) |
0.65 (1.00) |
0.902 (1.00) |
0.082 (1.00) |
0.62 (1.00) |
0.481 (1.00) |
0.474 (1.00) |
||
| FLG | 44 (26%) | 128 |
0.0194 (1.00) |
0.258 (1.00) |
0.728 (1.00) |
0.864 (1.00) |
1 (1.00) |
0.748 (1.00) |
0.132 (1.00) |
0.612 (1.00) |
0.0504 (1.00) |
1 (1.00) |
0.427 (1.00) |
||
| GPR112 | 35 (20%) | 137 |
0.682 (1.00) |
0.96 (1.00) |
0.569 (1.00) |
0.645 (1.00) |
0.364 (1.00) |
0.711 (1.00) |
0.256 (1.00) |
0.982 (1.00) |
0.645 (1.00) |
0.183 (1.00) |
0.458 (1.00) |
0.324 (1.00) |
|
| MUC7 | 15 (9%) | 157 |
0.299 (1.00) |
0.39 (1.00) |
0.0313 (1.00) |
0.742 (1.00) |
1 (1.00) |
0.547 (1.00) |
0.346 (1.00) |
0.542 (1.00) |
0.896 (1.00) |
0.593 (1.00) |
0.685 (1.00) |
||
| COL11A1 | 34 (20%) | 138 |
0.968 (1.00) |
0.824 (1.00) |
1 (1.00) |
0.0327 (1.00) |
0.2 (1.00) |
1 (1.00) |
0.623 (1.00) |
0.383 (1.00) |
0.468 (1.00) |
0.441 (1.00) |
0.649 (1.00) |
0.707 (1.00) |
|
| HRNR | 25 (15%) | 147 |
0.178 (1.00) |
0.216 (1.00) |
0.665 (1.00) |
0.0632 (1.00) |
0.689 (1.00) |
0.386 (1.00) |
0.722 (1.00) |
0.372 (1.00) |
0.521 (1.00) |
0.104 (1.00) |
0.696 (1.00) |
0.0121 (1.00) |
|
| BRAF | 15 (9%) | 157 |
0.851 (1.00) |
0.5 (1.00) |
0.287 (1.00) |
0.996 (1.00) |
1 (1.00) |
0.81 (1.00) |
0.491 (1.00) |
0.196 (1.00) |
0.837 (1.00) |
0.788 (1.00) |
0.161 (1.00) |
||
| PCK1 | 10 (6%) | 162 |
0.183 (1.00) |
0.319 (1.00) |
1 (1.00) |
0.999 (1.00) |
1 (1.00) |
0.517 (1.00) |
0.00122 (1.00) |
0.0881 (1.00) |
0.876 (1.00) |
0.141 (1.00) |
0.117 (1.00) |
||
| CSMD3 | 78 (45%) | 94 |
0.169 (1.00) |
0.413 (1.00) |
0.645 (1.00) |
0.756 (1.00) |
0.77 (1.00) |
0.229 (1.00) |
0.33 (1.00) |
0.165 (1.00) |
0.486 (1.00) |
0.0666 (1.00) |
0.968 (1.00) |
0.125 (1.00) |
|
| RB1 | 7 (4%) | 165 |
0.0814 (1.00) |
0.29 (1.00) |
0.25 (1.00) |
0.303 (1.00) |
1 (1.00) |
0.888 (1.00) |
0.961 (1.00) |
0.011 (1.00) |
0.954 (1.00) |
0.49 (1.00) |
0.745 (1.00) |
||
| RIMS2 | 32 (19%) | 140 |
0.56 (1.00) |
0.716 (1.00) |
0.239 (1.00) |
0.953 (1.00) |
0.815 (1.00) |
0.469 (1.00) |
0.319 (1.00) |
0.0367 (1.00) |
0.793 (1.00) |
0.847 (1.00) |
0.37 (1.00) |
0.508 (1.00) |
|
| RIT1 | 8 (5%) | 164 |
0.829 (1.00) |
0.303 (1.00) |
1 (1.00) |
0.971 (1.00) |
0.446 (1.00) |
0.351 (1.00) |
0.287 (1.00) |
0.195 (1.00) |
0.394 (1.00) |
0.0203 (1.00) |
0.502 (1.00) |
||
| FTSJD1 | 6 (3%) | 166 |
0.355 (1.00) |
0.837 (1.00) |
0.688 (1.00) |
1 (1.00) |
1 (1.00) |
0.587 (1.00) |
0.234 (1.00) |
0.709 (1.00) |
0.671 (1.00) |
1 (1.00) |
0.198 (1.00) |
||
| LRP1B | 61 (35%) | 111 |
0.197 (1.00) |
0.719 (1.00) |
0.263 (1.00) |
0.726 (1.00) |
0.849 (1.00) |
0.217 (1.00) |
0.337 (1.00) |
0.875 (1.00) |
0.901 (1.00) |
0.175 (1.00) |
0.176 (1.00) |
0.433 (1.00) |
|
| OR10J3 | 9 (5%) | 163 |
0.644 (1.00) |
0.945 (1.00) |
0.734 (1.00) |
0.976 (1.00) |
1 (1.00) |
0.8 (1.00) |
0.908 (1.00) |
0.613 (1.00) |
0.556 (1.00) |
1 (1.00) |
0.338 (1.00) |
||
| SETD2 | 15 (9%) | 157 |
0.0885 (1.00) |
0.518 (1.00) |
0.175 (1.00) |
0.994 (1.00) |
0.0733 (1.00) |
0.282 (1.00) |
0.417 (1.00) |
0.28 (1.00) |
0.896 (1.00) |
0.335 (1.00) |
0.409 (1.00) |
||
| LTBP1 | 20 (12%) | 152 |
0.221 (1.00) |
0.408 (1.00) |
0.638 (1.00) |
0.877 (1.00) |
1 (1.00) |
0.0046 (1.00) |
0.297 (1.00) |
0.219 (1.00) |
0.178 (1.00) |
0.649 (1.00) |
0.251 (1.00) |
||
| ZCCHC5 | 10 (6%) | 162 |
0.291 (1.00) |
0.615 (1.00) |
0.346 (1.00) |
0.885 (1.00) |
1 (1.00) |
0.598 (1.00) |
0.0232 (1.00) |
0.505 (1.00) |
0.871 (1.00) |
1 (1.00) |
0.231 (1.00) |
||
| ADAMTS5 | 14 (8%) | 158 |
0.00337 (1.00) |
0.4 (1.00) |
1 (1.00) |
0.985 (1.00) |
1 (1.00) |
0.899 (1.00) |
0.463 (1.00) |
0.347 (1.00) |
0.00413 (1.00) |
1 (1.00) |
0.106 (1.00) |
||
| ZNF268 | 5 (3%) | 167 |
0.235 (1.00) |
0.507 (1.00) |
0.181 (1.00) |
1 (1.00) |
1 (1.00) |
0.213 (1.00) |
0.437 (1.00) |
0.354 (1.00) |
0.996 (1.00) |
0.49 (1.00) |
0.58 (1.00) |
||
| OR4Q3 | 11 (6%) | 161 |
0.485 (1.00) |
0.635 (1.00) |
0.115 (1.00) |
0.694 (1.00) |
0.0314 (1.00) |
0.174 (1.00) |
0.263 (1.00) |
0.574 (1.00) |
0.54 (1.00) |
0.298 (1.00) |
|||
| SMAD4 | 7 (4%) | 165 |
0.807 (1.00) |
0.465 (1.00) |
1 (1.00) |
1 (1.00) |
0.403 (1.00) |
0.541 (1.00) |
0.0108 (1.00) |
0.725 (1.00) |
0.954 (1.00) |
1 (1.00) |
0.527 (1.00) |
||
| ARID1A | 11 (6%) | 161 |
0.48 (1.00) |
0.0113 (1.00) |
0.551 (1.00) |
0.994 (1.00) |
1 (1.00) |
0.175 (1.00) |
0.0382 (1.00) |
0.659 (1.00) |
0.517 (1.00) |
0.592 (1.00) |
0.91 (1.00) |
||
| CCDC73 | 11 (6%) | 161 |
0.317 (1.00) |
0.594 (1.00) |
0.551 (1.00) |
0.102 (1.00) |
1 (1.00) |
0.211 (1.00) |
0.656 (1.00) |
0.816 (1.00) |
0.564 (1.00) |
0.315 (1.00) |
0.426 (1.00) |
||
| MGA | 16 (9%) | 156 |
0.216 (1.00) |
0.0204 (1.00) |
0.437 (1.00) |
0.0315 (1.00) |
1 (1.00) |
0.742 (1.00) |
0.0879 (1.00) |
0.346 (1.00) |
0.207 (1.00) |
0.844 (1.00) |
0.253 (1.00) |
||
| IFNA7 | 5 (3%) | 167 |
0.444 (1.00) |
0.776 (1.00) |
0.662 (1.00) |
0.934 (1.00) |
1 (1.00) |
0.765 (1.00) |
0.38 (1.00) |
1 (1.00) |
0.306 (1.00) |
0.291 (1.00) |
0.0203 (1.00) |
||
| FANCD2 | 7 (4%) | 165 |
0.604 (1.00) |
0.409 (1.00) |
0.25 (1.00) |
1 (1.00) |
0.403 (1.00) |
0.929 (1.00) |
0.477 (1.00) |
0.251 (1.00) |
0.93 (1.00) |
1 (1.00) |
0.421 (1.00) |
||
| MBD1 | 6 (3%) | 166 |
0.578 (1.00) |
0.22 (1.00) |
1 (1.00) |
0.977 (1.00) |
1 (1.00) |
0.173 (1.00) |
0.96 (1.00) |
0.709 (1.00) |
0.671 (1.00) |
1 (1.00) |
0.0264 (1.00) |
||
| FAM48B1 | 10 (6%) | 162 |
0.832 (1.00) |
0.81 (1.00) |
0.111 (1.00) |
0.985 (1.00) |
0.525 (1.00) |
0.00191 (1.00) |
0.0797 (1.00) |
0.301 (1.00) |
0.263 (1.00) |
0.816 (1.00) |
0.705 (1.00) |
||
| FGB | 11 (6%) | 161 |
0.283 (1.00) |
0.583 (1.00) |
1 (1.00) |
0.988 (1.00) |
0.56 (1.00) |
0.949 (1.00) |
0.837 (1.00) |
1 (1.00) |
0.97 (1.00) |
0.00855 (1.00) |
0.0933 (1.00) |
||
| FLI1 | 6 (3%) | 166 |
0.345 (1.00) |
0.568 (1.00) |
0.688 (1.00) |
1 (1.00) |
0.356 (1.00) |
0.888 (1.00) |
0.765 (1.00) |
0.709 (1.00) |
0.671 (1.00) |
0.359 (1.00) |
0.213 (1.00) |
||
| LAX1 | 6 (3%) | 166 |
0.116 (1.00) |
0.442 (1.00) |
0.688 (1.00) |
1 (1.00) |
1 (1.00) |
0.438 (1.00) |
1 (1.00) |
0.671 (1.00) |
1 (1.00) |
0.579 (1.00) |
|||
| COL19A1 | 14 (8%) | 158 |
0.847 (1.00) |
0.273 (1.00) |
0.263 (1.00) |
0.0716 (1.00) |
0.000347 (0.593) |
0.602 (1.00) |
0.952 (1.00) |
0.676 (1.00) |
1 (1.00) |
0.976 (1.00) |
1 (1.00) |
0.456 (1.00) |
|
| MLL3 | 34 (20%) | 138 |
0.353 (1.00) |
0.565 (1.00) |
0.57 (1.00) |
0.548 (1.00) |
0.783 (1.00) |
0.707 (1.00) |
0.455 (1.00) |
0.834 (1.00) |
1 (1.00) |
0.358 (1.00) |
0.107 (1.00) |
0.989 (1.00) |
|
| OVCH1 | 14 (8%) | 158 |
0.305 (1.00) |
0.727 (1.00) |
0.171 (1.00) |
0.752 (1.00) |
0.602 (1.00) |
0.271 (1.00) |
0.327 (1.00) |
0.862 (1.00) |
0.925 (1.00) |
0.398 (1.00) |
0.13 (1.00) |
||
| LRRC32 | 11 (6%) | 161 |
0.854 (1.00) |
0.393 (1.00) |
0.551 (1.00) |
0.542 (1.00) |
0.56 (1.00) |
0.819 (1.00) |
0.685 (1.00) |
0.53 (1.00) |
0.967 (1.00) |
0.423 (1.00) |
0.938 (1.00) |
||
| ANP32C | 8 (5%) | 164 |
0.634 (1.00) |
0.477 (1.00) |
0.145 (1.00) |
0.338 (1.00) |
1 (1.00) |
0.146 (1.00) |
0.38 (1.00) |
1 (1.00) |
0.768 (1.00) |
1 (1.00) |
0.0214 (1.00) |
||
| OR10G9 | 10 (6%) | 162 |
0.908 (1.00) |
0.0973 (1.00) |
0.516 (1.00) |
0.989 (1.00) |
1 (1.00) |
0.489 (1.00) |
0.553 (1.00) |
0.634 (1.00) |
0.00079 (1.00) |
0.484 (1.00) |
0.354 (1.00) |
||
| MTTP | 6 (3%) | 166 |
0.911 (1.00) |
0.144 (1.00) |
0.415 (1.00) |
0.982 (1.00) |
0.356 (1.00) |
0.544 (1.00) |
0.145 (1.00) |
0.31 (1.00) |
0.981 (1.00) |
0.49 (1.00) |
0.281 (1.00) |
||
| RUFY2 | 7 (4%) | 165 |
0.0653 (1.00) |
0.906 (1.00) |
1 (1.00) |
0.999 (1.00) |
0.403 (1.00) |
0.462 (1.00) |
0.843 (1.00) |
0.026 (1.00) |
0.191 (1.00) |
1 (1.00) |
0.431 (1.00) |
||
| PJA1 | 8 (5%) | 164 |
0.116 (1.00) |
0.365 (1.00) |
0.728 (1.00) |
0.231 (1.00) |
1 (1.00) |
0.704 (1.00) |
0.808 (1.00) |
0.745 (1.00) |
0.849 (1.00) |
0.698 (1.00) |
0.59 (1.00) |
||
| KIAA1755 | 12 (7%) | 160 |
0.704 (1.00) |
0.382 (1.00) |
0.148 (1.00) |
0.476 (1.00) |
0.593 (1.00) |
0.42 (1.00) |
0.715 (1.00) |
1 (1.00) |
0.654 (1.00) |
0.262 (1.00) |
0.711 (1.00) |
||
| CNGA2 | 11 (6%) | 161 |
0.454 (1.00) |
0.344 (1.00) |
0.349 (1.00) |
0.157 (1.00) |
0.56 (1.00) |
0.85 (1.00) |
0.966 (1.00) |
1 (1.00) |
0.217 (1.00) |
0.788 (1.00) |
0.481 (1.00) |
||
| ASTN2 | 14 (8%) | 158 |
0.919 (1.00) |
0.753 (1.00) |
1 (1.00) |
0.000227 (0.388) |
1 (1.00) |
0.894 (1.00) |
0.888 (1.00) |
0.252 (1.00) |
0.925 (1.00) |
0.549 (1.00) |
0.392 (1.00) |
||
| STXBP5L | 12 (7%) | 160 |
0.119 (1.00) |
0.169 (1.00) |
0.148 (1.00) |
0.999 (1.00) |
1 (1.00) |
0.715 (1.00) |
0.286 (1.00) |
0.453 (1.00) |
0.447 (1.00) |
0.335 (1.00) |
0.31 (1.00) |
||
| TEX15 | 24 (14%) | 148 |
0.799 (1.00) |
0.346 (1.00) |
0.269 (1.00) |
0.821 (1.00) |
1 (1.00) |
0.396 (1.00) |
0.407 (1.00) |
1 (1.00) |
0.546 (1.00) |
0.402 (1.00) |
0.243 (1.00) |
||
| ELTD1 | 15 (9%) | 157 |
0.0619 (1.00) |
0.0391 (1.00) |
0.788 (1.00) |
0.143 (1.00) |
1 (1.00) |
0.811 (1.00) |
0.648 (1.00) |
0.542 (1.00) |
0.345 (1.00) |
0.413 (1.00) |
0.0755 (1.00) |
||
| DACT1 | 10 (6%) | 162 |
0.194 (1.00) |
0.378 (1.00) |
1 (1.00) |
0.581 (1.00) |
0.147 (1.00) |
0.225 (1.00) |
0.0671 (1.00) |
0.792 (1.00) |
0.00985 (1.00) |
1 (1.00) |
0.2 (1.00) |
||
| OR10R2 | 10 (6%) | 162 |
0.718 (1.00) |
0.618 (1.00) |
0.111 (1.00) |
0.44 (1.00) |
1 (1.00) |
0.308 (1.00) |
0.389 (1.00) |
1 (1.00) |
0.636 (1.00) |
1 (1.00) |
0.56 (1.00) |
||
| SUN1 | 8 (5%) | 164 |
0.222 (1.00) |
0.0684 (1.00) |
0.728 (1.00) |
1 (1.00) |
1 (1.00) |
0.24 (1.00) |
0.885 (1.00) |
0.294 (1.00) |
0.279 (1.00) |
1 (1.00) |
0.119 (1.00) |
||
| PABPC3 | 9 (5%) | 163 |
0.0736 (1.00) |
0.413 (1.00) |
0.51 (1.00) |
0.976 (1.00) |
0.487 (1.00) |
0.548 (1.00) |
0.354 (1.00) |
0.117 (1.00) |
0.74 (1.00) |
0.281 (1.00) |
0.198 (1.00) |
||
| TLR4 | 23 (13%) | 149 |
0.819 (1.00) |
0.837 (1.00) |
1 (1.00) |
0.651 (1.00) |
1 (1.00) |
0.719 (1.00) |
0.855 (1.00) |
0.393 (1.00) |
0.00991 (1.00) |
0.291 (1.00) |
0.123 (1.00) |
||
| THEMIS | 10 (6%) | 162 |
0.0737 (1.00) |
0.995 (1.00) |
0.516 (1.00) |
0.999 (1.00) |
1 (1.00) |
0.768 (1.00) |
0.753 (1.00) |
0.301 (1.00) |
0.62 (1.00) |
0.788 (1.00) |
0.461 (1.00) |
||
| GNG2 | 4 (2%) | 168 |
0.468 (1.00) |
0.13 (1.00) |
1 (1.00) |
0.689 (1.00) |
1 (1.00) |
0.449 (1.00) |
1 (1.00) |
0.872 (1.00) |
0.49 (1.00) |
0.77 (1.00) |
|||
| GATA3 | 6 (3%) | 166 |
0.0501 (1.00) |
0.0661 (1.00) |
0.415 (1.00) |
0.724 (1.00) |
0.356 (1.00) |
0.662 (1.00) |
0.892 (1.00) |
0.196 (1.00) |
0.658 (1.00) |
1 (1.00) |
0.368 (1.00) |
||
| APC | 10 (6%) | 162 |
0.00557 (1.00) |
0.867 (1.00) |
1 (1.00) |
0.999 (1.00) |
0.525 (1.00) |
0.454 (1.00) |
0.0604 (1.00) |
0.12 (1.00) |
0.455 (1.00) |
0.377 (1.00) |
0.48 (1.00) |
||
| SERPINB13 | 9 (5%) | 163 |
0.0482 (1.00) |
0.693 (1.00) |
0.181 (1.00) |
0.0709 (1.00) |
0.487 (1.00) |
0.967 (1.00) |
0.296 (1.00) |
1 (1.00) |
0.000551 (0.942) |
1 (1.00) |
0.644 (1.00) |
||
| PDGFA | 5 (3%) | 167 |
0.479 (1.00) |
0.911 (1.00) |
0.0191 (1.00) |
0.0207 (1.00) |
1 (1.00) |
0.793 (1.00) |
0.938 (1.00) |
1 (1.00) |
0.996 (1.00) |
0.396 (1.00) |
0.487 (1.00) |
||
| SCG2 | 8 (5%) | 164 |
0.3 (1.00) |
0.625 (1.00) |
0.145 (1.00) |
0.0329 (1.00) |
0.0989 (1.00) |
0.441 (1.00) |
0.978 (1.00) |
1 (1.00) |
0.394 (1.00) |
1 (1.00) |
0.436 (1.00) |
||
| OR6F1 | 10 (6%) | 162 |
0.297 (1.00) |
0.908 (1.00) |
1 (1.00) |
0.999 (1.00) |
1 (1.00) |
0.878 (1.00) |
0.957 (1.00) |
0.301 (1.00) |
0.466 (1.00) |
0.385 (1.00) |
0.495 (1.00) |
||
| BRE | 4 (2%) | 168 |
0.0556 (1.00) |
0.565 (1.00) |
0.334 (1.00) |
1 (1.00) |
1 (1.00) |
0.61 (1.00) |
0.919 (1.00) |
1 (1.00) |
0.648 (1.00) |
1 (1.00) |
0.303 (1.00) |
||
| C12ORF74 | 3 (2%) | 169 |
1 (1.00) |
0.384 (1.00) |
1 (1.00) |
1 (1.00) |
0.895 (1.00) |
0.131 (1.00) |
0.967 (1.00) |
||||||
| POF1B | 9 (5%) | 163 |
0.207 (1.00) |
0.992 (1.00) |
0.181 (1.00) |
0.959 (1.00) |
1 (1.00) |
0.283 (1.00) |
0.521 (1.00) |
0.34 (1.00) |
0.171 (1.00) |
0.64 (1.00) |
0.688 (1.00) |
||
| OR2F2 | 6 (3%) | 166 |
0.185 (1.00) |
0.418 (1.00) |
1 (1.00) |
1 (1.00) |
1 (1.00) |
0.000666 (1.00) |
0.0115 (1.00) |
1 (1.00) |
0.439 (1.00) |
0.49 (1.00) |
0.455 (1.00) |
||
| F8 | 15 (9%) | 157 |
0.752 (1.00) |
0.0209 (1.00) |
0.418 (1.00) |
0.249 (1.00) |
1 (1.00) |
0.105 (1.00) |
0.785 (1.00) |
0.449 (1.00) |
0.481 (1.00) |
1 (1.00) |
0.512 (1.00) |
||
| TSHZ3 | 25 (15%) | 147 |
0.058 (1.00) |
0.0269 (1.00) |
0.136 (1.00) |
0.279 (1.00) |
0.681 (1.00) |
0.218 (1.00) |
0.476 (1.00) |
0.0796 (1.00) |
0.416 (1.00) |
0.92 (1.00) |
0.347 (1.00) |
0.468 (1.00) |
|
| TBX21 | 7 (4%) | 165 |
0.549 (1.00) |
0.867 (1.00) |
0.126 (1.00) |
0.3 (1.00) |
1 (1.00) |
0.324 (1.00) |
0.286 (1.00) |
0.499 (1.00) |
0.974 (1.00) |
1 (1.00) |
0.394 (1.00) |
||
| GPR158 | 18 (10%) | 154 |
0.904 (1.00) |
0.623 (1.00) |
0.621 (1.00) |
0.976 (1.00) |
0.364 (1.00) |
0.197 (1.00) |
0.802 (1.00) |
1 (1.00) |
0.0475 (1.00) |
1 (1.00) |
0.508 (1.00) |
||
| DENND2A | 9 (5%) | 163 |
0.03 (1.00) |
0.466 (1.00) |
0.0819 (1.00) |
0.976 (1.00) |
1 (1.00) |
0.694 (1.00) |
0.668 (1.00) |
0.175 (1.00) |
0.87 (1.00) |
1 (1.00) |
0.0546 (1.00) |
||
| EPHB6 | 19 (11%) | 153 |
0.34 (1.00) |
0.197 (1.00) |
0.81 (1.00) |
0.803 (1.00) |
1 (1.00) |
0.413 (1.00) |
0.56 (1.00) |
0.175 (1.00) |
0.855 (1.00) |
0.508 (1.00) |
0.395 (1.00) |
||
| EPHA6 | 22 (13%) | 150 |
0.656 (1.00) |
0.666 (1.00) |
0.108 (1.00) |
0.953 (1.00) |
0.374 (1.00) |
0.654 (1.00) |
0.198 (1.00) |
0.714 (1.00) |
0.225 (1.00) |
0.757 (1.00) |
0.366 (1.00) |
0.791 (1.00) |
|
| TTC18 | 5 (3%) | 167 |
0.659 (1.00) |
0.888 (1.00) |
0.063 (1.00) |
0.0921 (1.00) |
0.307 (1.00) |
0.497 (1.00) |
0.0124 (1.00) |
0.0905 (1.00) |
0.191 (1.00) |
0.0399 (1.00) |
|||
| FSCB | 15 (9%) | 157 |
0.117 (1.00) |
0.356 (1.00) |
0.596 (1.00) |
0.0864 (1.00) |
0.0733 (1.00) |
0.314 (1.00) |
0.311 (1.00) |
1 (1.00) |
0.014 (1.00) |
1 (1.00) |
0.864 (1.00) |
||
| SPTA1 | 51 (30%) | 121 |
0.0323 (1.00) |
0.347 (1.00) |
0.738 (1.00) |
0.0327 (1.00) |
0.578 (1.00) |
0.513 (1.00) |
0.132 (1.00) |
0.189 (1.00) |
0.708 (1.00) |
0.0543 (1.00) |
0.866 (1.00) |
0.387 (1.00) |
|
| CTRC | 4 (2%) | 168 |
0.768 (1.00) |
0.987 (1.00) |
0.626 (1.00) |
0.997 (1.00) |
0.253 (1.00) |
0.569 (1.00) |
0.648 (1.00) |
1 (1.00) |
0.187 (1.00) |
||||
| TMTC1 | 22 (13%) | 150 |
0.188 (1.00) |
0.297 (1.00) |
0.0695 (1.00) |
0.132 (1.00) |
0.185 (1.00) |
0.646 (1.00) |
0.355 (1.00) |
0.29 (1.00) |
0.0949 (1.00) |
0.0901 (1.00) |
0.0955 (1.00) |
||
| ITGAX | 17 (10%) | 155 |
0.762 (1.00) |
0.436 (1.00) |
0.8 (1.00) |
0.269 (1.00) |
1 (1.00) |
0.278 (1.00) |
0.254 (1.00) |
0.589 (1.00) |
0.0317 (1.00) |
0.133 (1.00) |
0.0482 (1.00) |
||
| CDH6 | 17 (10%) | 155 |
0.327 (1.00) |
0.708 (1.00) |
1 (1.00) |
0.526 (1.00) |
0.611 (1.00) |
0.669 (1.00) |
0.0457 (1.00) |
0.774 (1.00) |
0.112 (1.00) |
0.0872 (1.00) |
0.847 (1.00) |
||
| NALCN | 24 (14%) | 148 |
0.168 (1.00) |
0.0114 (1.00) |
0.667 (1.00) |
0.736 (1.00) |
1 (1.00) |
0.882 (1.00) |
0.946 (1.00) |
0.456 (1.00) |
0.776 (1.00) |
0.521 (1.00) |
0.548 (1.00) |
||
| COL5A1 | 13 (8%) | 159 |
0.875 (1.00) |
0.122 (1.00) |
0.262 (1.00) |
0.697 (1.00) |
0.603 (1.00) |
0.514 (1.00) |
0.546 (1.00) |
0.33 (1.00) |
0.695 (1.00) |
0.428 (1.00) |
0.472 (1.00) |
||
| SVEP1 | 21 (12%) | 151 |
0.386 (1.00) |
0.855 (1.00) |
0.642 (1.00) |
0.646 (1.00) |
0.365 (1.00) |
0.404 (1.00) |
0.294 (1.00) |
0.897 (1.00) |
0.792 (1.00) |
0.231 (1.00) |
0.1 (1.00) |
||
| OR5I1 | 11 (6%) | 161 |
0.797 (1.00) |
0.872 (1.00) |
0.115 (1.00) |
0.36 (1.00) |
1 (1.00) |
0.0815 (1.00) |
0.93 (1.00) |
1 (1.00) |
0.574 (1.00) |
0.354 (1.00) |
0.124 (1.00) |
||
| EPS8L3 | 4 (2%) | 168 |
0.258 (1.00) |
0.978 (1.00) |
0.334 (1.00) |
1 (1.00) |
1 (1.00) |
0.569 (1.00) |
0.855 (1.00) |
1 (1.00) |
0.0314 (1.00) |
||||
| CYP1A1 | 4 (2%) | 168 |
0.961 (1.00) |
0.745 (1.00) |
0.626 (1.00) |
0.0241 (1.00) |
1 (1.00) |
1 (1.00) |
0.872 (1.00) |
1 (1.00) |
0.77 (1.00) |
||||
| DEFB112 | 4 (2%) | 168 |
0.963 (1.00) |
0.0831 (1.00) |
0.334 (1.00) |
0.0185 (1.00) |
0.0249 (1.00) |
0.185 (1.00) |
0.264 (1.00) |
0.276 (1.00) |
0.855 (1.00) |
1 (1.00) |
0.661 (1.00) |
||
| FBXL7 | 17 (10%) | 155 |
0.41 (1.00) |
0.326 (1.00) |
0.127 (1.00) |
0.248 (1.00) |
0.611 (1.00) |
0.688 (1.00) |
0.518 (1.00) |
0.501 (1.00) |
0.906 (1.00) |
0.649 (1.00) |
0.0905 (1.00) |
||
| TARS2 | 8 (5%) | 164 |
0.865 (1.00) |
0.518 (1.00) |
0.728 (1.00) |
1 (1.00) |
1 (1.00) |
0.314 (1.00) |
0.835 (1.00) |
0.564 (1.00) |
0.849 (1.00) |
0.127 (1.00) |
0.724 (1.00) |
||
| GPR174 | 6 (3%) | 166 |
0.407 (1.00) |
0.0533 (1.00) |
0.22 (1.00) |
0.00302 (1.00) |
1 (1.00) |
0.154 (1.00) |
0.137 (1.00) |
0.429 (1.00) |
0.658 (1.00) |
1 (1.00) |
0.348 (1.00) |
||
| HOXA5 | 6 (3%) | 166 |
0.12 (1.00) |
0.241 (1.00) |
0.0952 (1.00) |
0.977 (1.00) |
1 (1.00) |
0.0675 (1.00) |
0.851 (1.00) |
1 (1.00) |
0.671 (1.00) |
0.64 (1.00) |
0.613 (1.00) |
||
| SH2D2A | 6 (3%) | 166 |
0.581 (1.00) |
0.813 (1.00) |
0.688 (1.00) |
0.913 (1.00) |
1 (1.00) |
0.191 (1.00) |
0.709 (1.00) |
0.154 (1.00) |
0.253 (1.00) |
0.418 (1.00) |
|||
| ABCB5 | 19 (11%) | 153 |
0.468 (1.00) |
0.952 (1.00) |
0.332 (1.00) |
0.0379 (1.00) |
0.366 (1.00) |
0.0586 (1.00) |
0.462 (1.00) |
0.483 (1.00) |
0.0221 (1.00) |
0.466 (1.00) |
0.365 (1.00) |
||
| ANKRD56 | 11 (6%) | 161 |
0.362 (1.00) |
0.583 (1.00) |
0.756 (1.00) |
0.0264 (1.00) |
0.56 (1.00) |
0.458 (1.00) |
0.585 (1.00) |
1 (1.00) |
0.0039 (1.00) |
0.385 (1.00) |
0.12 (1.00) |
||
| GTF2I | 3 (2%) | 169 |
0.594 (1.00) |
0.00172 (1.00) |
1 (1.00) |
1 (1.00) |
0.43 (1.00) |
1 (1.00) |
0.0353 (1.00) |
||||||
| MUC16 | 79 (46%) | 93 |
0.709 (1.00) |
0.54 (1.00) |
0.358 (1.00) |
0.671 (1.00) |
0.42 (1.00) |
1 (1.00) |
0.0345 (1.00) |
0.708 (1.00) |
0.619 (1.00) |
0.379 (1.00) |
0.368 (1.00) |
0.463 (1.00) |
|
| VPS13C | 19 (11%) | 153 |
0.656 (1.00) |
0.46 (1.00) |
0.144 (1.00) |
0.468 (1.00) |
0.366 (1.00) |
0.786 (1.00) |
0.446 (1.00) |
0.789 (1.00) |
0.905 (1.00) |
0.579 (1.00) |
0.777 (1.00) |
||
| OR2T27 | 8 (5%) | 164 |
0.349 (1.00) |
0.665 (1.00) |
0.728 (1.00) |
0.997 (1.00) |
1 (1.00) |
0.387 (1.00) |
0.092 (1.00) |
1 (1.00) |
0.849 (1.00) |
1 (1.00) |
0.863 (1.00) |
||
| FERD3L | 7 (4%) | 165 |
0.0242 (1.00) |
0.166 (1.00) |
1 (1.00) |
1 (1.00) |
0.403 (1.00) |
0.645 (1.00) |
0.881 (1.00) |
0.709 (1.00) |
0.981 (1.00) |
0.291 (1.00) |
0.299 (1.00) |
||
| OR4C16 | 14 (8%) | 158 |
0.969 (1.00) |
0.521 (1.00) |
0.578 (1.00) |
0.00461 (1.00) |
0.602 (1.00) |
0.443 (1.00) |
0.885 (1.00) |
1 (1.00) |
0.62 (1.00) |
0.698 (1.00) |
0.474 (1.00) |
||
| C1ORF173 | 25 (15%) | 147 |
0.761 (1.00) |
0.153 (1.00) |
0.287 (1.00) |
0.852 (1.00) |
0.218 (1.00) |
0.57 (1.00) |
0.201 (1.00) |
0.823 (1.00) |
0.161 (1.00) |
1 (1.00) |
0.0575 (1.00) |
||
| KDM5C | 8 (5%) | 164 |
0.727 (1.00) |
0.757 (1.00) |
1 (1.00) |
0.644 (1.00) |
1 (1.00) |
0.136 (1.00) |
0.167 (1.00) |
0.0654 (1.00) |
0.979 (1.00) |
0.215 (1.00) |
0.106 (1.00) |
||
| KIF9 | 7 (4%) | 165 |
0.194 (1.00) |
0.17 (1.00) |
0.455 (1.00) |
0.303 (1.00) |
1 (1.00) |
0.174 (1.00) |
0.73 (1.00) |
1 (1.00) |
0.974 (1.00) |
1 (1.00) |
0.000941 (1.00) |
||
| BRS3 | 7 (4%) | 165 |
0.442 (1.00) |
0.186 (1.00) |
1 (1.00) |
0.994 (1.00) |
1 (1.00) |
0.14 (1.00) |
0.638 (1.00) |
0.725 (1.00) |
0.527 (1.00) |
0.484 (1.00) |
0.247 (1.00) |
||
| SIRPB1 | 6 (3%) | 166 |
0.0559 (1.00) |
0.914 (1.00) |
0.688 (1.00) |
0.0854 (1.00) |
1 (1.00) |
0.222 (1.00) |
0.514 (1.00) |
0.429 (1.00) |
0.277 (1.00) |
1 (1.00) |
0.2 (1.00) |
||
| RP1L1 | 32 (19%) | 140 |
0.278 (1.00) |
0.465 (1.00) |
1 (1.00) |
0.667 (1.00) |
0.699 (1.00) |
0.998 (1.00) |
0.0539 (1.00) |
0.793 (1.00) |
0.111 (1.00) |
0.524 (1.00) |
0.115 (1.00) |
||
| COL3A1 | 22 (13%) | 150 |
0.166 (1.00) |
0.454 (1.00) |
0.00561 (1.00) |
0.99 (1.00) |
0.368 (1.00) |
0.649 (1.00) |
0.0705 (1.00) |
0.659 (1.00) |
0.0942 (1.00) |
0.692 (1.00) |
0.772 (1.00) |
||
| LPPR4 | 14 (8%) | 158 |
0.829 (1.00) |
0.759 (1.00) |
0.578 (1.00) |
0.339 (1.00) |
1 (1.00) |
0.541 (1.00) |
0.447 (1.00) |
0.862 (1.00) |
0.55 (1.00) |
1 (1.00) |
0.602 (1.00) |
||
| HOXA3 | 6 (3%) | 166 |
0.403 (1.00) |
0.891 (1.00) |
0.415 (1.00) |
0.00211 (1.00) |
1 (1.00) |
0.491 (1.00) |
0.571 (1.00) |
0.429 (1.00) |
0.958 (1.00) |
1 (1.00) |
0.235 (1.00) |
||
| OR56A4 | 6 (3%) | 166 |
0.395 (1.00) |
0.725 (1.00) |
0.415 (1.00) |
1 (1.00) |
1 (1.00) |
0.911 (1.00) |
0.646 (1.00) |
1 (1.00) |
0.29 (1.00) |
1 (1.00) |
0.184 (1.00) |
||
| KDR | 20 (12%) | 152 |
0.206 (1.00) |
0.477 (1.00) |
0.638 (1.00) |
0.955 (1.00) |
0.471 (1.00) |
1 (1.00) |
0.256 (1.00) |
0.835 (1.00) |
0.567 (1.00) |
0.437 (1.00) |
0.898 (1.00) |
0.756 (1.00) |
|
| ANKRD44 | 9 (5%) | 163 |
0.18 (1.00) |
0.571 (1.00) |
0.734 (1.00) |
0.196 (1.00) |
1 (1.00) |
0.488 (1.00) |
0.467 (1.00) |
0.989 (1.00) |
0.17 (1.00) |
0.658 (1.00) |
|||
| MFSD8 | 5 (3%) | 167 |
0.677 (1.00) |
0.0896 (1.00) |
0.662 (1.00) |
1 (1.00) |
1 (1.00) |
0.528 (1.00) |
0.186 (1.00) |
1 (1.00) |
0.784 (1.00) |
1 (1.00) |
0.189 (1.00) |
||
| ZNF260 | 4 (2%) | 168 |
0.899 (1.00) |
0.919 (1.00) |
1 (1.00) |
0.997 (1.00) |
1 (1.00) |
0.532 (1.00) |
0.552 (1.00) |
1 (1.00) |
0.855 (1.00) |
0.061 (1.00) |
0.982 (1.00) |
||
| C1ORF49 | 6 (3%) | 166 |
0.805 (1.00) |
0.757 (1.00) |
0.415 (1.00) |
0.255 (1.00) |
0.194 (1.00) |
1 (1.00) |
0.124 (1.00) |
0.952 (1.00) |
0.429 (1.00) |
0.931 (1.00) |
0.291 (1.00) |
0.701 (1.00) |
|
| C9ORF64 | 3 (2%) | 169 |
0.216 (1.00) |
0.0501 (1.00) |
0.0949 (1.00) |
0.999 (1.00) |
1 (1.00) |
0.623 (1.00) |
1 (1.00) |
0.655 (1.00) |
0.812 (1.00) |
||||
| LELP1 | 3 (2%) | 169 |
0.732 (1.00) |
0.0949 (1.00) |
1 (1.00) |
1 (1.00) |
0.304 (1.00) |
0.881 (1.00) |
1 (1.00) |
0.655 (1.00) |
0.788 (1.00) |
||||
| TBX15 | 11 (6%) | 161 |
0.474 (1.00) |
0.697 (1.00) |
0.756 (1.00) |
0.0642 (1.00) |
0.56 (1.00) |
0.639 (1.00) |
0.871 (1.00) |
0.53 (1.00) |
0.00425 (1.00) |
0.639 (1.00) |
0.00193 (1.00) |
||
| AOAH | 8 (5%) | 164 |
0.668 (1.00) |
0.685 (1.00) |
0.291 (1.00) |
0.156 (1.00) |
1 (1.00) |
0.715 (1.00) |
0.297 (1.00) |
1 (1.00) |
0.000287 (0.491) |
0.315 (1.00) |
0.0509 (1.00) |
||
| STAC3 | 3 (2%) | 169 |
0.00289 (1.00) |
0.958 (1.00) |
1 (1.00) |
0.969 (1.00) |
1 (1.00) |
0.359 (1.00) |
0.0479 (1.00) |
0.43 (1.00) |
0.0277 (1.00) |
||||
| CD5L | 12 (7%) | 160 |
0.911 (1.00) |
0.928 (1.00) |
0.229 (1.00) |
0.653 (1.00) |
0.593 (1.00) |
0.781 (1.00) |
0.914 (1.00) |
1 (1.00) |
0.95 (1.00) |
0.747 (1.00) |
0.0937 (1.00) |
||
| GRK5 | 7 (4%) | 165 |
0.689 (1.00) |
0.304 (1.00) |
0.704 (1.00) |
0.303 (1.00) |
1 (1.00) |
0.109 (1.00) |
0.301 (1.00) |
0.725 (1.00) |
0.551 (1.00) |
0.64 (1.00) |
0.0769 (1.00) |
||
| C8ORF37 | 6 (3%) | 166 |
0.99 (1.00) |
0.0941 (1.00) |
1 (1.00) |
0.982 (1.00) |
1 (1.00) |
0.979 (1.00) |
0.954 (1.00) |
0.709 (1.00) |
0.745 (1.00) |
0.49 (1.00) |
0.441 (1.00) |
||
| PTH | 3 (2%) | 169 |
0.00662 (1.00) |
0.807 (1.00) |
1 (1.00) |
1 (1.00) |
1 (1.00) |
0.91 (1.00) |
0.841 (1.00) |
1 (1.00) |
0.00531 (1.00) |
1 (1.00) |
0.119 (1.00) |
||
| NAALAD2 | 9 (5%) | 163 |
0.37 (1.00) |
0.528 (1.00) |
0.734 (1.00) |
0.381 (1.00) |
0.487 (1.00) |
0.824 (1.00) |
0.484 (1.00) |
0.613 (1.00) |
0.000574 (0.981) |
0.484 (1.00) |
0.29 (1.00) |
||
| TAAR5 | 7 (4%) | 165 |
0.148 (1.00) |
0.462 (1.00) |
1 (1.00) |
0.0327 (1.00) |
0.999 (1.00) |
0.403 (1.00) |
0.049 (1.00) |
0.25 (1.00) |
0.251 (1.00) |
0.662 (1.00) |
1 (1.00) |
0.715 (1.00) |
|
| TRPC1 | 7 (4%) | 165 |
0.296 (1.00) |
0.817 (1.00) |
0.704 (1.00) |
0.835 (1.00) |
1 (1.00) |
0.172 (1.00) |
0.756 (1.00) |
0.725 (1.00) |
0.93 (1.00) |
0.127 (1.00) |
0.711 (1.00) |
||
| IL18RAP | 5 (3%) | 167 |
0.269 (1.00) |
0.272 (1.00) |
0.662 (1.00) |
1 (1.00) |
1 (1.00) |
0.862 (1.00) |
0.14 (1.00) |
0.297 (1.00) |
1 (1.00) |
0.29 (1.00) |
|||
| C2ORF39 | 8 (5%) | 164 |
0.913 (1.00) |
0.405 (1.00) |
0.728 (1.00) |
0.971 (1.00) |
1 (1.00) |
0.88 (1.00) |
0.403 (1.00) |
0.745 (1.00) |
0.602 (1.00) |
0.437 (1.00) |
0.452 (1.00) |
||
| ARID2 | 12 (7%) | 160 |
0.112 (1.00) |
0.0409 (1.00) |
1 (1.00) |
0.999 (1.00) |
0.593 (1.00) |
0.622 (1.00) |
0.155 (1.00) |
0.296 (1.00) |
0.432 (1.00) |
1 (1.00) |
0.494 (1.00) |
||
| SPEG | 16 (9%) | 156 |
0.205 (1.00) |
0.975 (1.00) |
0.193 (1.00) |
0.0891 (1.00) |
0.606 (1.00) |
0.926 (1.00) |
0.781 (1.00) |
0.346 (1.00) |
0.945 (1.00) |
0.428 (1.00) |
0.246 (1.00) |
||
| NHEDC1 | 9 (5%) | 163 |
0.185 (1.00) |
0.0899 (1.00) |
0.734 (1.00) |
0.000678 (1.00) |
1 (1.00) |
0.0254 (1.00) |
0.859 (1.00) |
0.467 (1.00) |
0.561 (1.00) |
1 (1.00) |
0.466 (1.00) |
||
| HAX1 | 4 (2%) | 168 |
0.464 (1.00) |
0.759 (1.00) |
0.626 (1.00) |
1 (1.00) |
1 (1.00) |
0.445 (1.00) |
0.333 (1.00) |
0.467 (1.00) |
0.916 (1.00) |
0.257 (1.00) |
|||
| ATM | 15 (9%) | 157 |
0.75 (1.00) |
0.331 (1.00) |
0.596 (1.00) |
0.813 (1.00) |
1 (1.00) |
0.471 (1.00) |
0.187 (1.00) |
0.871 (1.00) |
0.875 (1.00) |
1 (1.00) |
0.665 (1.00) |
||
| IL1RAPL1 | 11 (6%) | 161 |
0.652 (1.00) |
0.446 (1.00) |
0.229 (1.00) |
0.973 (1.00) |
1 (1.00) |
0.924 (1.00) |
0.216 (1.00) |
0.659 (1.00) |
0.781 (1.00) |
1 (1.00) |
0.564 (1.00) |
||
| AQP10 | 6 (3%) | 166 |
0.0743 (1.00) |
0.00134 (1.00) |
0.688 (1.00) |
0.0606 (1.00) |
0.356 (1.00) |
0.96 (1.00) |
0.166 (1.00) |
0.709 (1.00) |
0.931 (1.00) |
0.315 (1.00) |
0.701 (1.00) |
||
| OR4A15 | 14 (8%) | 158 |
0.506 (1.00) |
0.289 (1.00) |
0.414 (1.00) |
0.793 (1.00) |
1 (1.00) |
0.332 (1.00) |
0.782 (1.00) |
0.622 (1.00) |
0.00641 (1.00) |
0.829 (1.00) |
0.908 (1.00) |
||
| OR2G2 | 12 (7%) | 160 |
0.797 (1.00) |
0.376 (1.00) |
0.774 (1.00) |
0.653 (1.00) |
0.199 (1.00) |
0.62 (1.00) |
0.782 (1.00) |
0.685 (1.00) |
0.556 (1.00) |
1 (1.00) |
0.737 (1.00) |
||
| CXCL6 | 4 (2%) | 168 |
0.597 (1.00) |
0.981 (1.00) |
1 (1.00) |
1 (1.00) |
1 (1.00) |
0.869 (1.00) |
0.569 (1.00) |
0.872 (1.00) |
1 (1.00) |
0.257 (1.00) |
|||
| BTK | 7 (4%) | 165 |
0.181 (1.00) |
0.483 (1.00) |
0.455 (1.00) |
0.994 (1.00) |
1 (1.00) |
0.93 (1.00) |
0.229 (1.00) |
0.725 (1.00) |
0.551 (1.00) |
1 (1.00) |
0.627 (1.00) |
||
| OLAH | 7 (4%) | 165 |
0.519 (1.00) |
0.255 (1.00) |
0.704 (1.00) |
0.2 (1.00) |
0.403 (1.00) |
0.0403 (1.00) |
0.715 (1.00) |
0.725 (1.00) |
0.93 (1.00) |
1 (1.00) |
0.0125 (1.00) |
||
| DYDC2 | 3 (2%) | 169 |
0.342 (1.00) |
0.385 (1.00) |
0.0949 (1.00) |
1 (1.00) |
1 (1.00) |
1 (1.00) |
0.655 (1.00) |
1 (1.00) |
0.812 (1.00) |
||||
| DGKB | 11 (6%) | 161 |
0.323 (1.00) |
0.24 (1.00) |
0.756 (1.00) |
0.659 (1.00) |
0.56 (1.00) |
0.134 (1.00) |
0.433 (1.00) |
0.816 (1.00) |
0.339 (1.00) |
0.571 (1.00) |
0.546 (1.00) |
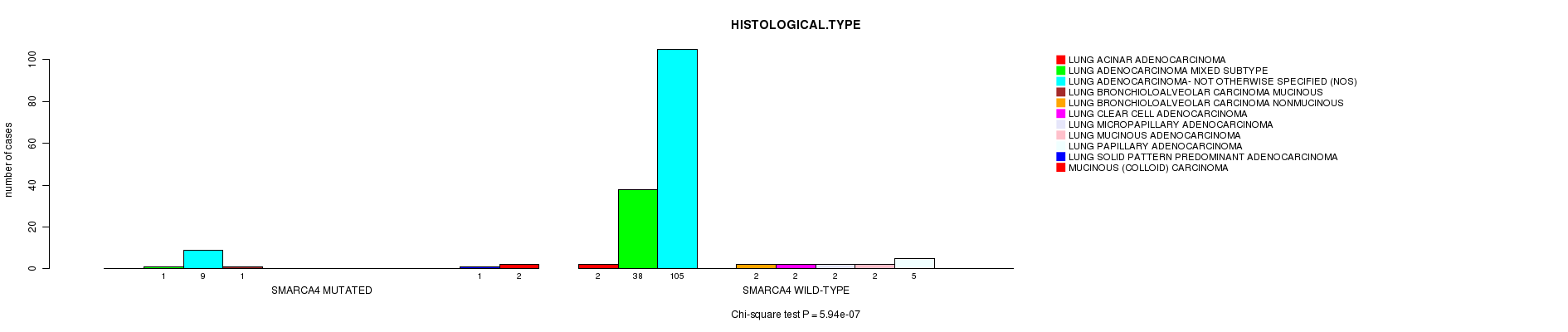
P value = 5.94e-07 (Chi-square test), Q value = 0.001
Table S1. Gene #12: 'SMARCA4 MUTATION STATUS' versus Clinical Feature #5: 'HISTOLOGICAL.TYPE'
| nPatients | LUNG ACINAR ADENOCARCINOMA | LUNG ADENOCARCINOMA MIXED SUBTYPE | LUNG ADENOCARCINOMA- NOT OTHERWISE SPECIFIED (NOS) | LUNG BRONCHIOLOALVEOLAR CARCINOMA MUCINOUS | LUNG BRONCHIOLOALVEOLAR CARCINOMA NONMUCINOUS | LUNG CLEAR CELL ADENOCARCINOMA | LUNG MICROPAPILLARY ADENOCARCINOMA | LUNG MUCINOUS ADENOCARCINOMA | LUNG PAPILLARY ADENOCARCINOMA | LUNG SOLID PATTERN PREDOMINANT ADENOCARCINOMA | MUCINOUS (COLLOID) CARCINOMA |
|---|---|---|---|---|---|---|---|---|---|---|---|
| ALL | 2 | 39 | 114 | 1 | 2 | 2 | 2 | 2 | 5 | 1 | 2 |
| SMARCA4 MUTATED | 0 | 1 | 9 | 1 | 0 | 0 | 0 | 0 | 0 | 1 | 2 |
| SMARCA4 WILD-TYPE | 2 | 38 | 105 | 0 | 2 | 2 | 2 | 2 | 5 | 0 | 0 |
Figure S1. Get High-res Image Gene #12: 'SMARCA4 MUTATION STATUS' versus Clinical Feature #5: 'HISTOLOGICAL.TYPE'
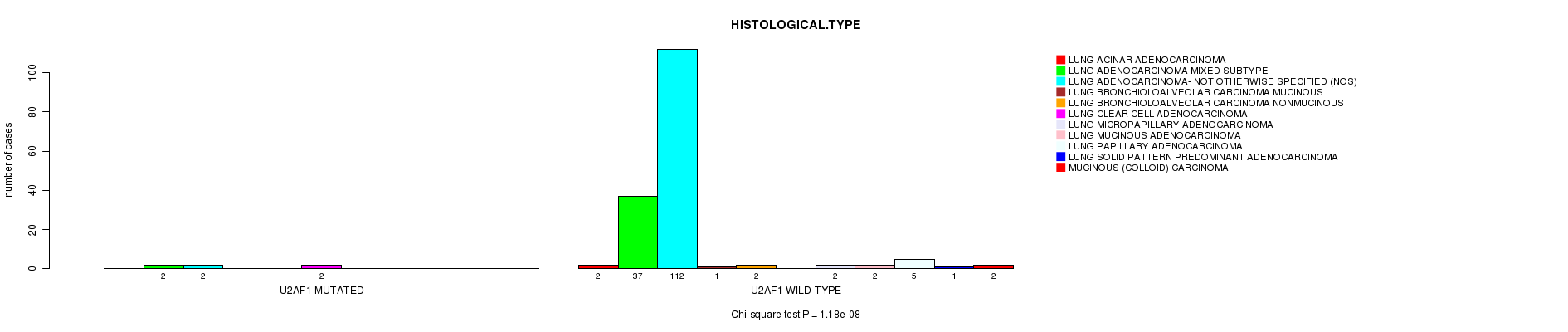
P value = 1.18e-08 (Chi-square test), Q value = 2e-05
Table S2. Gene #17: 'U2AF1 MUTATION STATUS' versus Clinical Feature #5: 'HISTOLOGICAL.TYPE'
| nPatients | LUNG ACINAR ADENOCARCINOMA | LUNG ADENOCARCINOMA MIXED SUBTYPE | LUNG ADENOCARCINOMA- NOT OTHERWISE SPECIFIED (NOS) | LUNG BRONCHIOLOALVEOLAR CARCINOMA MUCINOUS | LUNG BRONCHIOLOALVEOLAR CARCINOMA NONMUCINOUS | LUNG CLEAR CELL ADENOCARCINOMA | LUNG MICROPAPILLARY ADENOCARCINOMA | LUNG MUCINOUS ADENOCARCINOMA | LUNG PAPILLARY ADENOCARCINOMA | LUNG SOLID PATTERN PREDOMINANT ADENOCARCINOMA | MUCINOUS (COLLOID) CARCINOMA |
|---|---|---|---|---|---|---|---|---|---|---|---|
| ALL | 2 | 39 | 114 | 1 | 2 | 2 | 2 | 2 | 5 | 1 | 2 |
| U2AF1 MUTATED | 0 | 2 | 2 | 0 | 0 | 2 | 0 | 0 | 0 | 0 | 0 |
| U2AF1 WILD-TYPE | 2 | 37 | 112 | 1 | 2 | 0 | 2 | 2 | 5 | 1 | 2 |
Figure S2. Get High-res Image Gene #17: 'U2AF1 MUTATION STATUS' versus Clinical Feature #5: 'HISTOLOGICAL.TYPE'
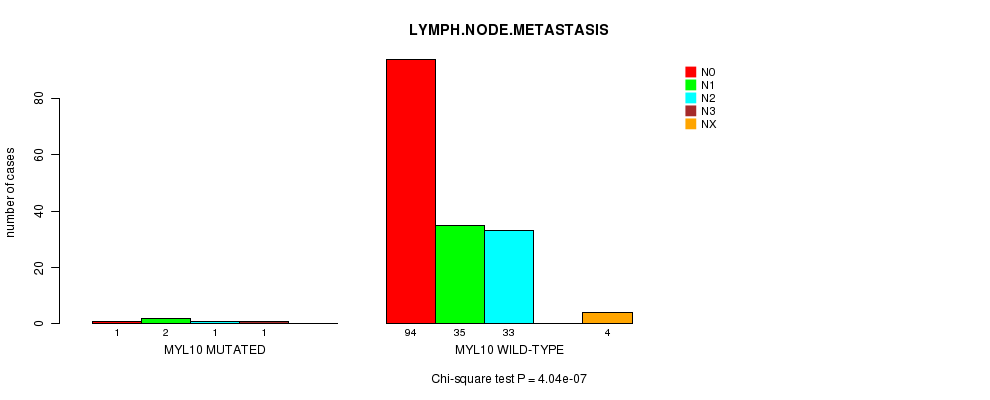
P value = 4.04e-07 (Chi-square test), Q value = 7e-04
Table S3. Gene #29: 'MYL10 MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
| nPatients | N0 | N1 | N2 | N3 | NX |
|---|---|---|---|---|---|
| ALL | 95 | 37 | 34 | 1 | 4 |
| MYL10 MUTATED | 1 | 2 | 1 | 1 | 0 |
| MYL10 WILD-TYPE | 94 | 35 | 33 | 0 | 4 |
Figure S3. Get High-res Image Gene #29: 'MYL10 MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
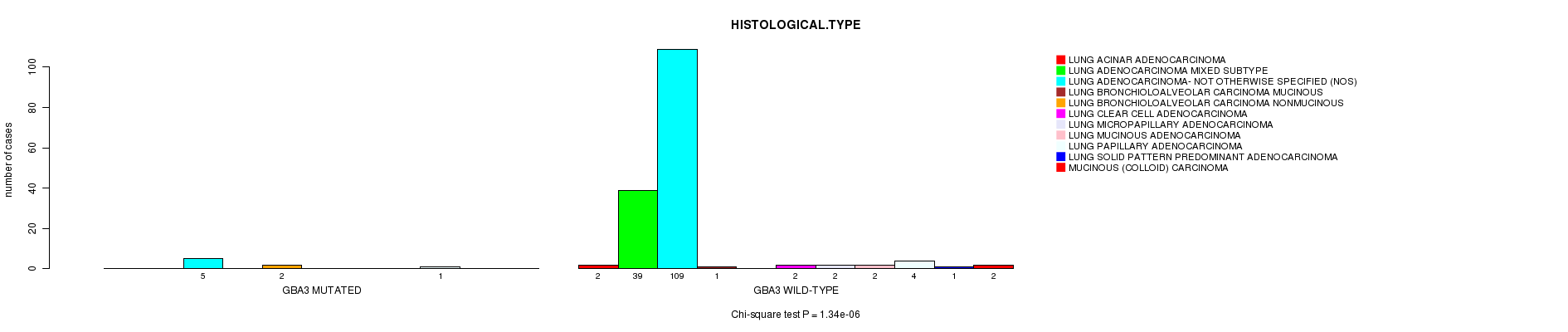
P value = 1.34e-06 (Chi-square test), Q value = 0.0023
Table S4. Gene #30: 'GBA3 MUTATION STATUS' versus Clinical Feature #5: 'HISTOLOGICAL.TYPE'
| nPatients | LUNG ACINAR ADENOCARCINOMA | LUNG ADENOCARCINOMA MIXED SUBTYPE | LUNG ADENOCARCINOMA- NOT OTHERWISE SPECIFIED (NOS) | LUNG BRONCHIOLOALVEOLAR CARCINOMA MUCINOUS | LUNG BRONCHIOLOALVEOLAR CARCINOMA NONMUCINOUS | LUNG CLEAR CELL ADENOCARCINOMA | LUNG MICROPAPILLARY ADENOCARCINOMA | LUNG MUCINOUS ADENOCARCINOMA | LUNG PAPILLARY ADENOCARCINOMA | LUNG SOLID PATTERN PREDOMINANT ADENOCARCINOMA | MUCINOUS (COLLOID) CARCINOMA |
|---|---|---|---|---|---|---|---|---|---|---|---|
| ALL | 2 | 39 | 114 | 1 | 2 | 2 | 2 | 2 | 5 | 1 | 2 |
| GBA3 MUTATED | 0 | 0 | 5 | 0 | 2 | 0 | 0 | 0 | 1 | 0 | 0 |
| GBA3 WILD-TYPE | 2 | 39 | 109 | 1 | 0 | 2 | 2 | 2 | 4 | 1 | 2 |
Figure S4. Get High-res Image Gene #30: 'GBA3 MUTATION STATUS' versus Clinical Feature #5: 'HISTOLOGICAL.TYPE'
P value = 5.04e-05 (Chi-square test), Q value = 0.086
Table S5. Gene #41: 'SVOP MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
| nPatients | N0 | N1 | N2 | N3 | NX |
|---|---|---|---|---|---|
| ALL | 95 | 37 | 34 | 1 | 4 |
| SVOP MUTATED | 2 | 2 | 2 | 1 | 0 |
| SVOP WILD-TYPE | 93 | 35 | 32 | 0 | 4 |
Figure S5. Get High-res Image Gene #41: 'SVOP MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
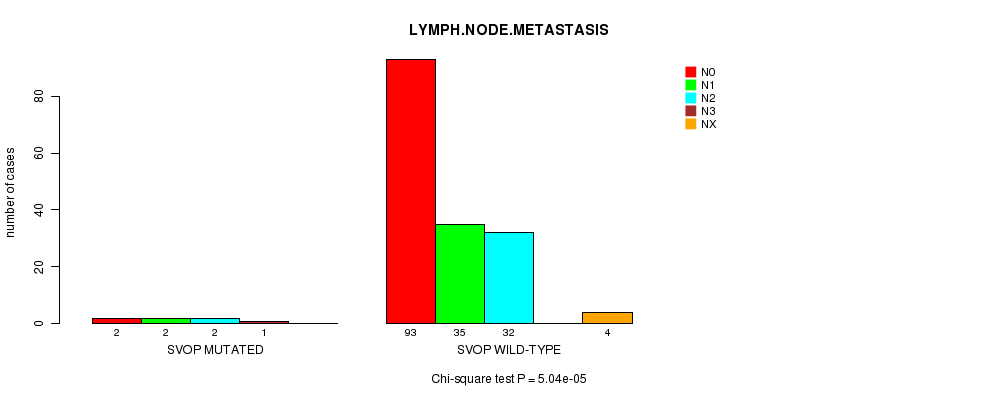
P value = 1.48e-05 (Chi-square test), Q value = 0.025
Table S6. Gene #62: 'KRT28 MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
| nPatients | N0 | N1 | N2 | N3 | NX |
|---|---|---|---|---|---|
| ALL | 95 | 37 | 34 | 1 | 4 |
| KRT28 MUTATED | 1 | 3 | 2 | 1 | 0 |
| KRT28 WILD-TYPE | 94 | 34 | 32 | 0 | 4 |
Figure S6. Get High-res Image Gene #62: 'KRT28 MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
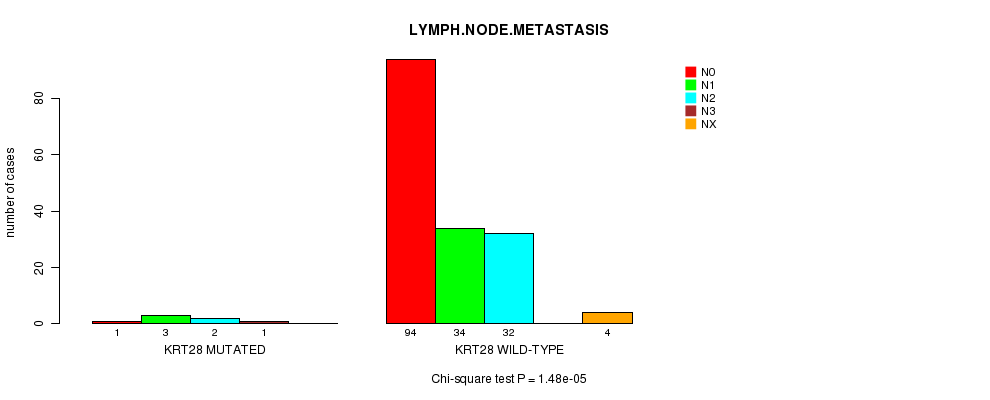
P value = 4.72e-06 (Chi-square test), Q value = 0.0081
Table S7. Gene #82: 'SPATA18 MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
| nPatients | N0 | N1 | N2 | N3 | NX |
|---|---|---|---|---|---|
| ALL | 95 | 37 | 34 | 1 | 4 |
| SPATA18 MUTATED | 1 | 5 | 1 | 1 | 0 |
| SPATA18 WILD-TYPE | 94 | 32 | 33 | 0 | 4 |
Figure S7. Get High-res Image Gene #82: 'SPATA18 MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
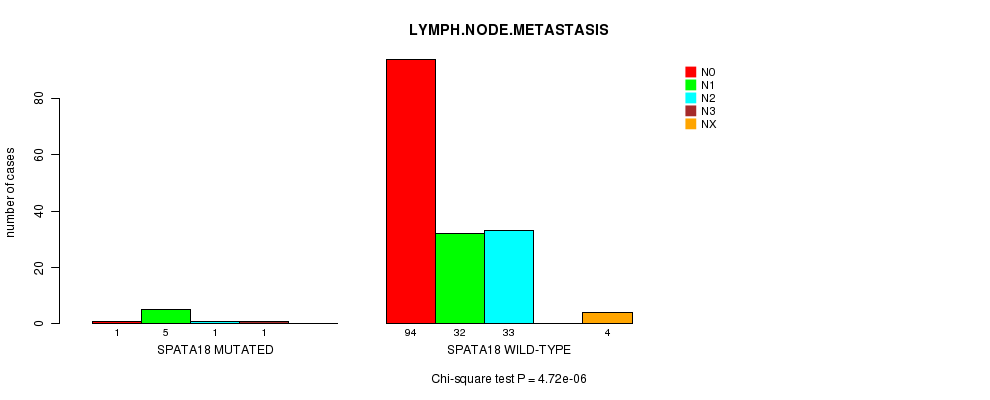
P value = 1.38e-05 (Chi-square test), Q value = 0.024
Table S8. Gene #115: 'HCK MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
| nPatients | N0 | N1 | N2 | N3 | NX |
|---|---|---|---|---|---|
| ALL | 95 | 37 | 34 | 1 | 4 |
| HCK MUTATED | 3 | 1 | 1 | 1 | 0 |
| HCK WILD-TYPE | 92 | 36 | 33 | 0 | 4 |
Figure S8. Get High-res Image Gene #115: 'HCK MUTATION STATUS' versus Clinical Feature #10: 'LYMPH.NODE.METASTASIS'
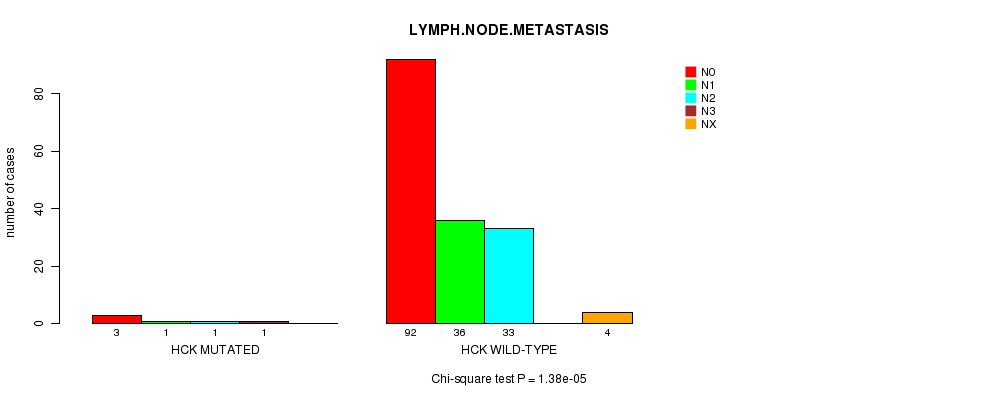
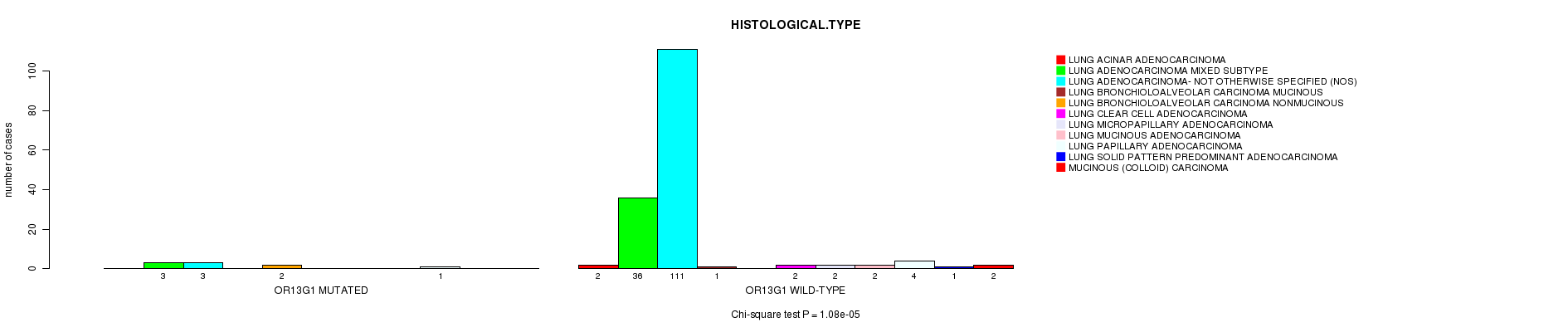
P value = 1.08e-05 (Chi-square test), Q value = 0.018
Table S9. Gene #146: 'OR13G1 MUTATION STATUS' versus Clinical Feature #5: 'HISTOLOGICAL.TYPE'
| nPatients | LUNG ACINAR ADENOCARCINOMA | LUNG ADENOCARCINOMA MIXED SUBTYPE | LUNG ADENOCARCINOMA- NOT OTHERWISE SPECIFIED (NOS) | LUNG BRONCHIOLOALVEOLAR CARCINOMA MUCINOUS | LUNG BRONCHIOLOALVEOLAR CARCINOMA NONMUCINOUS | LUNG CLEAR CELL ADENOCARCINOMA | LUNG MICROPAPILLARY ADENOCARCINOMA | LUNG MUCINOUS ADENOCARCINOMA | LUNG PAPILLARY ADENOCARCINOMA | LUNG SOLID PATTERN PREDOMINANT ADENOCARCINOMA | MUCINOUS (COLLOID) CARCINOMA |
|---|---|---|---|---|---|---|---|---|---|---|---|
| ALL | 2 | 39 | 114 | 1 | 2 | 2 | 2 | 2 | 5 | 1 | 2 |
| OR13G1 MUTATED | 0 | 3 | 3 | 0 | 2 | 0 | 0 | 0 | 1 | 0 | 0 |
| OR13G1 WILD-TYPE | 2 | 36 | 111 | 1 | 0 | 2 | 2 | 2 | 4 | 1 | 2 |
Figure S9. Get High-res Image Gene #146: 'OR13G1 MUTATION STATUS' versus Clinical Feature #5: 'HISTOLOGICAL.TYPE'
-
Mutation data file = LUAD-TP.mutsig.cluster.txt
-
Clinical data file = LUAD-TP.clin.merged.picked.txt
-
Number of patients = 172
-
Number of significantly mutated genes = 158
-
Number of selected clinical features = 13
-
Exclude genes that fewer than K tumors have mutations, K = 3
For survival clinical features, the Kaplan-Meier survival curves of tumors with and without gene mutations were plotted and the statistical significance P values were estimated by logrank test (Bland and Altman 2004) using the 'survdiff' function in R
For continuous numerical clinical features, two-tailed Student's t test with unequal variance (Lehmann and Romano 2005) was applied to compare the clinical values between tumors with and without gene mutations using 't.test' function in R
For binary or multi-class clinical features (nominal or ordinal), two-tailed Fisher's exact tests (Fisher 1922) were used to estimate the P values using the 'fisher.test' function in R
For multi-class clinical features (nominal or ordinal), Chi-square tests (Greenwood and Nikulin 1996) were used to estimate the P values using the 'chisq.test' function in R
For multiple hypothesis correction, Q value is the False Discovery Rate (FDR) analogue of the P value (Benjamini and Hochberg 1995), defined as the minimum FDR at which the test may be called significant. We used the 'Benjamini and Hochberg' method of 'p.adjust' function in R to convert P values into Q values.
This is an experimental feature. The full results of the analysis summarized in this report can be downloaded from the TCGA Data Coordination Center.