This pipeline computes the correlation between significant copy number variation (cnv focal) genes and selected clinical features.
Testing the association between copy number variation 70 focal events and 12 clinical features across 278 patients, one significant finding detected with Q value < 0.25.
-
del_22q13.32 cnv correlated to 'PATHOLOGY.M.STAGE'.
Table 1. Get Full Table Overview of the association between significant copy number variation of 70 focal events and 12 clinical features. Shown in the table are P values (Q values). Thresholded by Q value < 0.25, one significant finding detected.
|
Clinical Features |
Time to Death |
AGE |
NEOPLASM DISEASESTAGE |
PATHOLOGY T STAGE |
PATHOLOGY N STAGE |
PATHOLOGY M STAGE |
GENDER |
KARNOFSKY PERFORMANCE SCORE |
NUMBERPACKYEARSSMOKED |
NUMBER OF LYMPH NODES |
RACE | ETHNICITY | ||
| nCNV (%) | nWild-Type | logrank test | Wilcoxon-test | Fisher's exact test | Fisher's exact test | Fisher's exact test | Fisher's exact test | Fisher's exact test | Wilcoxon-test | Wilcoxon-test | Wilcoxon-test | Fisher's exact test | Fisher's exact test | |
| del 22q13 32 | 121 (44%) | 157 |
0.283 (1.00) |
0.164 (1.00) |
0.142 (1.00) |
0.254 (1.00) |
0.0602 (1.00) |
8e-05 (0.0672) |
1 (1.00) |
0.0654 (1.00) |
0.966 (1.00) |
0.126 (1.00) |
0.0546 (1.00) |
0.655 (1.00) |
| amp 1p34 2 | 66 (24%) | 212 |
0.9 (1.00) |
0.0605 (1.00) |
0.162 (1.00) |
0.336 (1.00) |
0.467 (1.00) |
0.789 (1.00) |
1 (1.00) |
0.363 (1.00) |
0.266 (1.00) |
0.673 (1.00) |
0.177 (1.00) |
1 (1.00) |
| amp 1q21 3 | 130 (47%) | 148 |
0.0473 (1.00) |
0.145 (1.00) |
0.00548 (1.00) |
0.831 (1.00) |
0.00931 (1.00) |
0.0881 (1.00) |
0.687 (1.00) |
0.307 (1.00) |
0.11 (1.00) |
0.0205 (1.00) |
0.288 (1.00) |
1 (1.00) |
| amp 1q23 3 | 140 (50%) | 138 |
0.436 (1.00) |
0.0164 (1.00) |
0.0252 (1.00) |
0.5 (1.00) |
0.00472 (1.00) |
0.062 (1.00) |
0.228 (1.00) |
0.344 (1.00) |
0.222 (1.00) |
0.093 (1.00) |
0.092 (1.00) |
1 (1.00) |
| amp 2p25 1 | 98 (35%) | 180 |
0.855 (1.00) |
0.0151 (1.00) |
0.00862 (1.00) |
0.86 (1.00) |
0.00237 (1.00) |
0.854 (1.00) |
0.123 (1.00) |
0.766 (1.00) |
0.097 (1.00) |
0.00947 (1.00) |
0.302 (1.00) |
0.172 (1.00) |
| amp 3p25 2 | 124 (45%) | 154 |
0.713 (1.00) |
0.0222 (1.00) |
0.177 (1.00) |
0.209 (1.00) |
0.0202 (1.00) |
1 (1.00) |
0.015 (1.00) |
0.123 (1.00) |
0.543 (1.00) |
0.0137 (1.00) |
0.105 (1.00) |
0.0688 (1.00) |
| amp 3q26 33 | 141 (51%) | 137 |
0.631 (1.00) |
0.333 (1.00) |
0.884 (1.00) |
0.941 (1.00) |
0.0689 (1.00) |
1 (1.00) |
0.688 (1.00) |
0.164 (1.00) |
0.519 (1.00) |
0.247 (1.00) |
0.301 (1.00) |
1 (1.00) |
| amp 4p16 3 | 56 (20%) | 222 |
0.0399 (1.00) |
0.958 (1.00) |
0.00897 (1.00) |
0.0112 (1.00) |
0.0826 (1.00) |
0.0325 (1.00) |
0.739 (1.00) |
0.0514 (1.00) |
0.642 (1.00) |
0.11 (1.00) |
0.0299 (1.00) |
0.242 (1.00) |
| amp 4q13 3 | 42 (15%) | 236 |
0.422 (1.00) |
0.454 (1.00) |
0.164 (1.00) |
0.236 (1.00) |
0.58 (1.00) |
0.798 (1.00) |
0.0602 (1.00) |
0.851 (1.00) |
0.933 (1.00) |
0.457 (1.00) |
0.749 (1.00) |
0.545 (1.00) |
| amp 5p15 33 | 135 (49%) | 143 |
0.758 (1.00) |
0.247 (1.00) |
0.822 (1.00) |
0.883 (1.00) |
0.994 (1.00) |
0.127 (1.00) |
0.592 (1.00) |
0.127 (1.00) |
0.254 (1.00) |
0.395 (1.00) |
0.314 (1.00) |
1 (1.00) |
| amp 6p22 3 | 102 (37%) | 176 |
0.287 (1.00) |
0.33 (1.00) |
0.0237 (1.00) |
0.106 (1.00) |
0.083 (1.00) |
0.804 (1.00) |
0.406 (1.00) |
0.538 (1.00) |
0.845 (1.00) |
0.652 (1.00) |
0.831 (1.00) |
1 (1.00) |
| amp 6q21 | 21 (8%) | 257 |
0.25 (1.00) |
0.912 (1.00) |
0.497 (1.00) |
0.544 (1.00) |
0.274 (1.00) |
0.273 (1.00) |
0.453 (1.00) |
0.398 (1.00) |
0.358 (1.00) |
0.316 (1.00) |
1 (1.00) |
1 (1.00) |
| amp 6q23 3 | 29 (10%) | 249 |
0.866 (1.00) |
0.373 (1.00) |
0.644 (1.00) |
0.717 (1.00) |
0.2 (1.00) |
0.524 (1.00) |
0.272 (1.00) |
0.94 (1.00) |
0.819 (1.00) |
0.882 (1.00) |
0.443 (1.00) |
1 (1.00) |
| amp 7p21 1 | 136 (49%) | 142 |
0.793 (1.00) |
0.154 (1.00) |
0.117 (1.00) |
0.398 (1.00) |
0.03 (1.00) |
0.705 (1.00) |
0.505 (1.00) |
0.442 (1.00) |
0.238 (1.00) |
0.153 (1.00) |
0.0179 (1.00) |
0.37 (1.00) |
| amp 7p11 2 | 130 (47%) | 148 |
0.845 (1.00) |
0.0375 (1.00) |
0.394 (1.00) |
0.809 (1.00) |
0.011 (1.00) |
0.944 (1.00) |
1 (1.00) |
0.665 (1.00) |
0.494 (1.00) |
0.105 (1.00) |
0.0627 (1.00) |
0.377 (1.00) |
| amp 8p11 23 | 80 (29%) | 198 |
0.368 (1.00) |
0.806 (1.00) |
0.523 (1.00) |
0.434 (1.00) |
0.761 (1.00) |
0.965 (1.00) |
0.378 (1.00) |
0.802 (1.00) |
0.314 (1.00) |
0.934 (1.00) |
0.844 (1.00) |
0.617 (1.00) |
| amp 8q22 3 | 171 (62%) | 107 |
0.351 (1.00) |
0.323 (1.00) |
0.911 (1.00) |
0.738 (1.00) |
0.184 (1.00) |
0.561 (1.00) |
0.582 (1.00) |
0.366 (1.00) |
0.52 (1.00) |
0.201 (1.00) |
0.362 (1.00) |
0.395 (1.00) |
| amp 9p24 1 | 57 (21%) | 221 |
0.517 (1.00) |
0.302 (1.00) |
0.895 (1.00) |
0.888 (1.00) |
0.616 (1.00) |
0.113 (1.00) |
0.621 (1.00) |
0.205 (1.00) |
0.217 (1.00) |
0.752 (1.00) |
0.0945 (1.00) |
1 (1.00) |
| amp 10p14 | 116 (42%) | 162 |
0.28 (1.00) |
0.0249 (1.00) |
0.447 (1.00) |
0.969 (1.00) |
0.163 (1.00) |
0.837 (1.00) |
1 (1.00) |
0.339 (1.00) |
0.434 (1.00) |
0.536 (1.00) |
0.756 (1.00) |
0.651 (1.00) |
| amp 11p13 | 34 (12%) | 244 |
0.0459 (1.00) |
0.832 (1.00) |
0.675 (1.00) |
0.811 (1.00) |
0.00799 (1.00) |
0.116 (1.00) |
1 (1.00) |
0.312 (1.00) |
0.611 (1.00) |
0.331 (1.00) |
0.488 (1.00) |
0.491 (1.00) |
| amp 11q13 3 | 103 (37%) | 175 |
0.316 (1.00) |
0.0235 (1.00) |
0.736 (1.00) |
0.583 (1.00) |
0.552 (1.00) |
0.124 (1.00) |
0.891 (1.00) |
0.505 (1.00) |
0.588 (1.00) |
0.917 (1.00) |
0.0455 (1.00) |
0.655 (1.00) |
| amp 11q22 2 | 51 (18%) | 227 |
0.394 (1.00) |
0.0442 (1.00) |
0.795 (1.00) |
0.804 (1.00) |
0.318 (1.00) |
0.317 (1.00) |
0.863 (1.00) |
0.421 (1.00) |
0.14 (1.00) |
0.788 (1.00) |
0.0398 (1.00) |
1 (1.00) |
| amp 12p12 1 | 85 (31%) | 193 |
0.73 (1.00) |
0.0086 (1.00) |
0.145 (1.00) |
0.215 (1.00) |
0.626 (1.00) |
0.299 (1.00) |
0.885 (1.00) |
0.789 (1.00) |
0.65 (1.00) |
0.252 (1.00) |
0.886 (1.00) |
1 (1.00) |
| amp 12q15 | 78 (28%) | 200 |
0.483 (1.00) |
0.0773 (1.00) |
0.757 (1.00) |
0.551 (1.00) |
0.485 (1.00) |
0.373 (1.00) |
0.551 (1.00) |
0.89 (1.00) |
0.596 (1.00) |
0.491 (1.00) |
0.461 (1.00) |
1 (1.00) |
| amp 13q22 1 | 83 (30%) | 195 |
0.756 (1.00) |
0.017 (1.00) |
0.762 (1.00) |
0.79 (1.00) |
0.562 (1.00) |
0.52 (1.00) |
0.107 (1.00) |
0.37 (1.00) |
0.92 (1.00) |
0.369 (1.00) |
0.232 (1.00) |
0.326 (1.00) |
| amp 16p13 2 | 60 (22%) | 218 |
0.327 (1.00) |
0.441 (1.00) |
0.33 (1.00) |
0.0232 (1.00) |
0.0679 (1.00) |
0.0598 (1.00) |
0.872 (1.00) |
0.451 (1.00) |
0.786 (1.00) |
0.284 (1.00) |
0.516 (1.00) |
0.587 (1.00) |
| amp 16p11 2 | 71 (26%) | 207 |
0.268 (1.00) |
0.476 (1.00) |
0.0353 (1.00) |
0.041 (1.00) |
0.00956 (1.00) |
0.168 (1.00) |
0.759 (1.00) |
0.13 (1.00) |
0.242 (1.00) |
0.06 (1.00) |
0.229 (1.00) |
0.335 (1.00) |
| amp 16q22 1 | 76 (27%) | 202 |
0.274 (1.00) |
0.164 (1.00) |
0.43 (1.00) |
0.027 (1.00) |
0.268 (1.00) |
0.0307 (1.00) |
0.0975 (1.00) |
0.548 (1.00) |
0.38 (1.00) |
0.875 (1.00) |
0.124 (1.00) |
0.33 (1.00) |
| amp 17p11 2 | 61 (22%) | 217 |
0.0375 (1.00) |
0.219 (1.00) |
0.441 (1.00) |
0.663 (1.00) |
0.0312 (1.00) |
0.246 (1.00) |
0.519 (1.00) |
0.0586 (1.00) |
0.86 (1.00) |
0.0415 (1.00) |
0.479 (1.00) |
0.588 (1.00) |
| amp 17q11 2 | 122 (44%) | 156 |
0.19 (1.00) |
0.285 (1.00) |
0.0749 (1.00) |
0.911 (1.00) |
0.0198 (1.00) |
0.52 (1.00) |
0.501 (1.00) |
0.239 (1.00) |
0.506 (1.00) |
0.0231 (1.00) |
0.433 (1.00) |
1 (1.00) |
| amp 17q12 | 112 (40%) | 166 |
0.0355 (1.00) |
0.12 (1.00) |
0.375 (1.00) |
0.238 (1.00) |
0.103 (1.00) |
0.445 (1.00) |
0.891 (1.00) |
0.276 (1.00) |
0.679 (1.00) |
0.103 (1.00) |
0.605 (1.00) |
1 (1.00) |
| amp 17q23 3 | 132 (47%) | 146 |
0.21 (1.00) |
0.215 (1.00) |
0.0497 (1.00) |
0.509 (1.00) |
0.0423 (1.00) |
0.71 (1.00) |
0.421 (1.00) |
0.308 (1.00) |
0.519 (1.00) |
0.024 (1.00) |
1 (1.00) |
1 (1.00) |
| amp 19q12 | 108 (39%) | 170 |
0.243 (1.00) |
0.371 (1.00) |
0.461 (1.00) |
0.864 (1.00) |
0.253 (1.00) |
0.809 (1.00) |
0.492 (1.00) |
0.668 (1.00) |
0.249 (1.00) |
0.0836 (1.00) |
0.808 (1.00) |
1 (1.00) |
| amp 19q13 43 | 101 (36%) | 177 |
0.547 (1.00) |
0.355 (1.00) |
0.319 (1.00) |
0.144 (1.00) |
0.106 (1.00) |
0.51 (1.00) |
0.58 (1.00) |
0.695 (1.00) |
0.693 (1.00) |
0.0363 (1.00) |
1 (1.00) |
0.66 (1.00) |
| amp 20q11 21 | 173 (62%) | 105 |
0.598 (1.00) |
0.25 (1.00) |
0.433 (1.00) |
0.984 (1.00) |
0.318 (1.00) |
0.807 (1.00) |
0.411 (1.00) |
0.789 (1.00) |
0.222 (1.00) |
0.575 (1.00) |
0.129 (1.00) |
0.387 (1.00) |
| amp 22q12 2 | 53 (19%) | 225 |
0.473 (1.00) |
0.684 (1.00) |
0.366 (1.00) |
0.539 (1.00) |
0.497 (1.00) |
1 (1.00) |
0.733 (1.00) |
0.399 (1.00) |
0.894 (1.00) |
0.103 (1.00) |
0.647 (1.00) |
1 (1.00) |
| del 1p36 11 | 56 (20%) | 222 |
0.501 (1.00) |
0.749 (1.00) |
0.323 (1.00) |
0.31 (1.00) |
0.00979 (1.00) |
0.914 (1.00) |
1 (1.00) |
0.697 (1.00) |
0.814 (1.00) |
0.245 (1.00) |
0.594 (1.00) |
0.587 (1.00) |
| del 1q32 1 | 50 (18%) | 228 |
0.288 (1.00) |
0.56 (1.00) |
0.178 (1.00) |
0.761 (1.00) |
0.189 (1.00) |
0.857 (1.00) |
0.0539 (1.00) |
0.936 (1.00) |
0.148 (1.00) |
0.0917 (1.00) |
1 (1.00) |
0.226 (1.00) |
| del 2q22 1 | 88 (32%) | 190 |
0.494 (1.00) |
0.901 (1.00) |
0.701 (1.00) |
0.296 (1.00) |
0.272 (1.00) |
0.674 (1.00) |
0.197 (1.00) |
0.773 (1.00) |
0.2 (1.00) |
0.146 (1.00) |
0.528 (1.00) |
0.652 (1.00) |
| del 2q34 | 110 (40%) | 168 |
0.567 (1.00) |
0.883 (1.00) |
0.201 (1.00) |
0.748 (1.00) |
0.0384 (1.00) |
0.739 (1.00) |
0.584 (1.00) |
0.962 (1.00) |
0.997 (1.00) |
0.157 (1.00) |
0.265 (1.00) |
1 (1.00) |
| del 2q37 1 | 137 (49%) | 141 |
0.294 (1.00) |
0.648 (1.00) |
0.0119 (1.00) |
0.844 (1.00) |
0.00348 (1.00) |
0.596 (1.00) |
0.14 (1.00) |
0.947 (1.00) |
0.352 (1.00) |
0.0317 (1.00) |
0.421 (1.00) |
0.2 (1.00) |
| del 3p14 2 | 79 (28%) | 199 |
0.453 (1.00) |
0.451 (1.00) |
0.303 (1.00) |
0.414 (1.00) |
0.0458 (1.00) |
0.143 (1.00) |
0.139 (1.00) |
0.0356 (1.00) |
0.397 (1.00) |
0.606 (1.00) |
0.00712 (1.00) |
0.614 (1.00) |
| del 4q22 1 | 104 (37%) | 174 |
0.78 (1.00) |
0.332 (1.00) |
0.524 (1.00) |
0.231 (1.00) |
0.805 (1.00) |
0.86 (1.00) |
0.581 (1.00) |
0.0958 (1.00) |
0.768 (1.00) |
0.358 (1.00) |
0.668 (1.00) |
0.654 (1.00) |
| del 4q34 2 | 118 (42%) | 160 |
0.4 (1.00) |
0.54 (1.00) |
0.327 (1.00) |
0.172 (1.00) |
0.159 (1.00) |
0.432 (1.00) |
1 (1.00) |
0.406 (1.00) |
0.218 (1.00) |
0.301 (1.00) |
0.514 (1.00) |
0.653 (1.00) |
| del 5q12 1 | 136 (49%) | 142 |
0.247 (1.00) |
0.00562 (1.00) |
0.132 (1.00) |
0.703 (1.00) |
0.0229 (1.00) |
0.361 (1.00) |
0.689 (1.00) |
0.0822 (1.00) |
0.97 (1.00) |
0.0579 (1.00) |
0.322 (1.00) |
1 (1.00) |
| del 6p25 3 | 68 (24%) | 210 |
0.47 (1.00) |
0.918 (1.00) |
0.436 (1.00) |
0.0397 (1.00) |
0.0139 (1.00) |
0.964 (1.00) |
0.351 (1.00) |
0.132 (1.00) |
0.803 (1.00) |
0.111 (1.00) |
0.0462 (1.00) |
0.6 (1.00) |
| del 6q21 | 130 (47%) | 148 |
0.782 (1.00) |
0.0917 (1.00) |
0.038 (1.00) |
0.912 (1.00) |
0.025 (1.00) |
0.111 (1.00) |
0.227 (1.00) |
0.119 (1.00) |
0.54 (1.00) |
0.00979 (1.00) |
0.761 (1.00) |
0.189 (1.00) |
| del 6q27 | 128 (46%) | 150 |
0.853 (1.00) |
0.367 (1.00) |
0.0381 (1.00) |
0.721 (1.00) |
0.00365 (1.00) |
0.0657 (1.00) |
0.505 (1.00) |
0.154 (1.00) |
0.396 (1.00) |
0.00498 (1.00) |
0.76 (1.00) |
0.181 (1.00) |
| del 7q36 3 | 39 (14%) | 239 |
0.631 (1.00) |
0.947 (1.00) |
0.912 (1.00) |
0.736 (1.00) |
0.454 (1.00) |
0.0755 (1.00) |
0.849 (1.00) |
0.929 (1.00) |
0.527 (1.00) |
0.495 (1.00) |
0.863 (1.00) |
0.534 (1.00) |
| del 8p23 1 | 156 (56%) | 122 |
0.962 (1.00) |
0.065 (1.00) |
0.0205 (1.00) |
0.537 (1.00) |
0.0576 (1.00) |
0.106 (1.00) |
0.419 (1.00) |
0.347 (1.00) |
0.287 (1.00) |
0.223 (1.00) |
0.0496 (1.00) |
0.177 (1.00) |
| del 9p23 | 120 (43%) | 158 |
0.426 (1.00) |
0.766 (1.00) |
0.834 (1.00) |
0.969 (1.00) |
0.704 (1.00) |
0.863 (1.00) |
1 (1.00) |
0.397 (1.00) |
0.344 (1.00) |
0.857 (1.00) |
0.637 (1.00) |
1 (1.00) |
| del 9p21 3 | 159 (57%) | 119 |
0.971 (1.00) |
0.0654 (1.00) |
0.95 (1.00) |
0.791 (1.00) |
0.478 (1.00) |
0.942 (1.00) |
1 (1.00) |
0.422 (1.00) |
0.877 (1.00) |
0.74 (1.00) |
0.467 (1.00) |
0.655 (1.00) |
| del 9q33 2 | 110 (40%) | 168 |
0.75 (1.00) |
0.17 (1.00) |
0.503 (1.00) |
1 (1.00) |
0.669 (1.00) |
0.566 (1.00) |
0.411 (1.00) |
0.398 (1.00) |
0.0362 (1.00) |
0.598 (1.00) |
0.93 (1.00) |
1 (1.00) |
| del 10p11 21 | 47 (17%) | 231 |
0.885 (1.00) |
0.77 (1.00) |
0.921 (1.00) |
0.172 (1.00) |
0.0355 (1.00) |
0.517 (1.00) |
0.858 (1.00) |
0.956 (1.00) |
0.675 (1.00) |
0.81 (1.00) |
0.00319 (1.00) |
0.593 (1.00) |
| del 10q23 31 | 110 (40%) | 168 |
0.41 (1.00) |
0.0576 (1.00) |
0.066 (1.00) |
0.687 (1.00) |
0.108 (1.00) |
0.499 (1.00) |
0.892 (1.00) |
0.142 (1.00) |
0.489 (1.00) |
0.129 (1.00) |
0.0936 (1.00) |
1 (1.00) |
| del 11p15 5 | 133 (48%) | 145 |
0.522 (1.00) |
0.0166 (1.00) |
0.0146 (1.00) |
0.725 (1.00) |
0.0574 (1.00) |
0.267 (1.00) |
0.893 (1.00) |
0.153 (1.00) |
0.961 (1.00) |
0.0202 (1.00) |
0.183 (1.00) |
1 (1.00) |
| del 11q23 3 | 95 (34%) | 183 |
0.861 (1.00) |
0.453 (1.00) |
0.472 (1.00) |
0.304 (1.00) |
0.265 (1.00) |
0.53 (1.00) |
1 (1.00) |
0.379 (1.00) |
0.94 (1.00) |
0.621 (1.00) |
0.414 (1.00) |
0.176 (1.00) |
| del 11q25 | 88 (32%) | 190 |
0.773 (1.00) |
0.588 (1.00) |
0.403 (1.00) |
0.307 (1.00) |
0.739 (1.00) |
0.607 (1.00) |
0.886 (1.00) |
0.306 (1.00) |
0.802 (1.00) |
0.608 (1.00) |
0.145 (1.00) |
0.328 (1.00) |
| del 12p13 1 | 43 (15%) | 235 |
0.554 (1.00) |
0.995 (1.00) |
0.326 (1.00) |
0.792 (1.00) |
0.118 (1.00) |
0.803 (1.00) |
0.461 (1.00) |
0.222 (1.00) |
0.0923 (1.00) |
0.165 (1.00) |
0.775 (1.00) |
0.584 (1.00) |
| del 12q24 33 | 58 (21%) | 220 |
0.227 (1.00) |
0.487 (1.00) |
0.00254 (1.00) |
0.245 (1.00) |
0.272 (1.00) |
0.615 (1.00) |
0.192 (1.00) |
0.85 (1.00) |
0.262 (1.00) |
0.0288 (1.00) |
0.0793 (1.00) |
0.587 (1.00) |
| del 13q14 2 | 103 (37%) | 175 |
0.632 (1.00) |
0.117 (1.00) |
0.267 (1.00) |
0.276 (1.00) |
0.136 (1.00) |
0.382 (1.00) |
0.579 (1.00) |
0.455 (1.00) |
0.206 (1.00) |
0.293 (1.00) |
0.0494 (1.00) |
1 (1.00) |
| del 14q24 1 | 87 (31%) | 191 |
0.705 (1.00) |
0.509 (1.00) |
0.213 (1.00) |
0.883 (1.00) |
0.0041 (1.00) |
0.772 (1.00) |
0.39 (1.00) |
0.464 (1.00) |
0.249 (1.00) |
0.144 (1.00) |
0.888 (1.00) |
0.645 (1.00) |
| del 15q13 1 | 109 (39%) | 169 |
0.363 (1.00) |
0.543 (1.00) |
0.674 (1.00) |
0.29 (1.00) |
0.59 (1.00) |
0.00935 (1.00) |
1 (1.00) |
0.202 (1.00) |
0.154 (1.00) |
0.737 (1.00) |
0.0694 (1.00) |
0.0734 (1.00) |
| del 16p13 3 | 113 (41%) | 165 |
0.335 (1.00) |
0.0966 (1.00) |
0.253 (1.00) |
0.0874 (1.00) |
0.0111 (1.00) |
0.0159 (1.00) |
0.683 (1.00) |
0.473 (1.00) |
0.976 (1.00) |
0.419 (1.00) |
0.0332 (1.00) |
1 (1.00) |
| del 16q23 1 | 77 (28%) | 201 |
0.684 (1.00) |
0.482 (1.00) |
0.743 (1.00) |
0.76 (1.00) |
0.214 (1.00) |
0.0869 (1.00) |
0.072 (1.00) |
0.0321 (1.00) |
0.308 (1.00) |
0.254 (1.00) |
0.507 (1.00) |
0.622 (1.00) |
| del 17p12 | 138 (50%) | 140 |
0.86 (1.00) |
0.13 (1.00) |
0.463 (1.00) |
0.897 (1.00) |
0.303 (1.00) |
0.82 (1.00) |
0.789 (1.00) |
0.827 (1.00) |
0.765 (1.00) |
0.351 (1.00) |
0.815 (1.00) |
0.675 (1.00) |
| del 18q23 | 114 (41%) | 164 |
0.0227 (1.00) |
0.129 (1.00) |
0.565 (1.00) |
0.441 (1.00) |
0.946 (1.00) |
0.349 (1.00) |
1 (1.00) |
0.697 (1.00) |
0.549 (1.00) |
0.661 (1.00) |
1 (1.00) |
0.4 (1.00) |
| del 19p13 3 | 98 (35%) | 180 |
0.273 (1.00) |
0.418 (1.00) |
0.019 (1.00) |
0.0221 (1.00) |
0.0188 (1.00) |
0.00438 (1.00) |
0.483 (1.00) |
0.0665 (1.00) |
0.987 (1.00) |
0.154 (1.00) |
0.209 (1.00) |
0.35 (1.00) |
| del xp11 3 | 63 (23%) | 215 |
0.732 (1.00) |
0.371 (1.00) |
0.914 (1.00) |
0.465 (1.00) |
0.652 (1.00) |
0.847 (1.00) |
0.523 (1.00) |
0.679 (1.00) |
0.284 (1.00) |
0.939 (1.00) |
0.708 (1.00) |
1 (1.00) |
| del xq21 33 | 55 (20%) | 223 |
0.292 (1.00) |
0.667 (1.00) |
0.809 (1.00) |
0.661 (1.00) |
0.967 (1.00) |
0.33 (1.00) |
0.614 (1.00) |
0.978 (1.00) |
0.791 (1.00) |
0.996 (1.00) |
0.0833 (1.00) |
0.249 (1.00) |
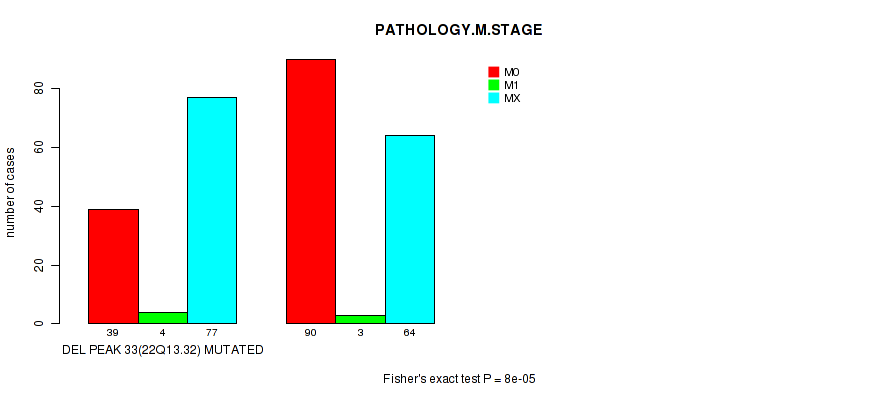
P value = 8e-05 (Fisher's exact test), Q value = 0.067
Table S1. Gene #68: 'del_22q13.32' versus Clinical Feature #6: 'PATHOLOGY.M.STAGE'
| nPatients | M0 | M1 | MX |
|---|---|---|---|
| ALL | 129 | 7 | 141 |
| DEL PEAK 33(22Q13.32) MUTATED | 39 | 4 | 77 |
| DEL PEAK 33(22Q13.32) WILD-TYPE | 90 | 3 | 64 |
Figure S1. Get High-res Image Gene #68: 'del_22q13.32' versus Clinical Feature #6: 'PATHOLOGY.M.STAGE'
-
Copy number data file = transformed.cor.cli.txt
-
Clinical data file = BLCA-TP.merged_data.txt
-
Number of patients = 278
-
Number of significantly focal cnvs = 70
-
Number of selected clinical features = 12
-
Exclude genes that fewer than K tumors have mutations, K = 3
For survival clinical features, the Kaplan-Meier survival curves of tumors with and without gene mutations were plotted and the statistical significance P values were estimated by logrank test (Bland and Altman 2004) using the 'survdiff' function in R
For binary or multi-class clinical features (nominal or ordinal), two-tailed Fisher's exact tests (Fisher 1922) were used to estimate the P values using the 'fisher.test' function in R
For multiple hypothesis correction, Q value is the False Discovery Rate (FDR) analogue of the P value (Benjamini and Hochberg 1995), defined as the minimum FDR at which the test may be called significant. We used the 'Benjamini and Hochberg' method of 'p.adjust' function in R to convert P values into Q values.
In addition to the links below, the full results of the analysis summarized in this report can also be downloaded programmatically using firehose_get, or interactively from either the Broad GDAC website or TCGA Data Coordination Center Portal.