(All_Metastatic cohort)
This pipeline computes the correlation between significantly recurrent gene mutations and molecular subtypes.
Testing the association between mutation status of 114 genes and 8 molecular subtypes across 228 patients, 2 significant findings detected with P value < 0.05 and Q value < 0.25.
-
BRAF mutation correlated to 'CN_CNMF' and 'MRNASEQ_CHIERARCHICAL'.
Table 1. Get Full Table Overview of the association between mutation status of 114 genes and 8 molecular subtypes. Shown in the table are P values (Q values). Thresholded by P value < 0.05 and Q value < 0.25, 2 significant findings detected.
|
Clinical Features |
CN CNMF |
METHLYATION CNMF |
RPPA CNMF |
RPPA CHIERARCHICAL |
MRNASEQ CNMF |
MRNASEQ CHIERARCHICAL |
MIRSEQ CNMF |
MIRSEQ CHIERARCHICAL |
||
| nMutated (%) | nWild-Type | Fisher's exact test | Fisher's exact test | Fisher's exact test | Chi-square test | Fisher's exact test | Fisher's exact test | Fisher's exact test | Fisher's exact test | |
| BRAF | 117 (51%) | 111 |
2.22e-07 (0.000201) |
0.0586 (1.00) |
0.0311 (1.00) |
0.00983 (1.00) |
0.0314 (1.00) |
8.88e-05 (0.0804) |
0.231 (1.00) |
0.154 (1.00) |
| TP53 | 35 (15%) | 193 |
0.143 (1.00) |
0.0271 (1.00) |
0.314 (1.00) |
0.138 (1.00) |
0.225 (1.00) |
0.458 (1.00) |
0.376 (1.00) |
0.121 (1.00) |
| C15ORF23 | 14 (6%) | 214 |
0.128 (1.00) |
0.263 (1.00) |
0.86 (1.00) |
0.826 (1.00) |
0.784 (1.00) |
1 (1.00) |
0.776 (1.00) |
0.779 (1.00) |
| CDKN2A | 33 (14%) | 195 |
0.11 (1.00) |
0.26 (1.00) |
0.374 (1.00) |
0.789 (1.00) |
0.89 (1.00) |
0.479 (1.00) |
0.74 (1.00) |
0.731 (1.00) |
| NRAS | 67 (29%) | 161 |
0.000531 (0.48) |
0.084 (1.00) |
0.0923 (1.00) |
0.329 (1.00) |
0.966 (1.00) |
0.858 (1.00) |
0.85 (1.00) |
0.829 (1.00) |
| OXA1L | 7 (3%) | 221 |
0.437 (1.00) |
0.434 (1.00) |
0.615 (1.00) |
0.472 (1.00) |
0.503 (1.00) |
0.276 (1.00) |
0.618 (1.00) |
0.627 (1.00) |
| STK19 | 11 (5%) | 217 |
0.737 (1.00) |
0.147 (1.00) |
0.224 (1.00) |
0.999 (1.00) |
0.861 (1.00) |
0.362 (1.00) |
0.577 (1.00) |
0.605 (1.00) |
| PTEN | 18 (8%) | 210 |
0.643 (1.00) |
0.214 (1.00) |
0.149 (1.00) |
0.131 (1.00) |
0.908 (1.00) |
0.0625 (1.00) |
0.819 (1.00) |
0.323 (1.00) |
| RAC1 | 17 (7%) | 211 |
0.631 (1.00) |
0.772 (1.00) |
0.94 (1.00) |
0.47 (1.00) |
0.512 (1.00) |
0.849 (1.00) |
0.582 (1.00) |
0.321 (1.00) |
| IDH1 | 12 (5%) | 216 |
0.311 (1.00) |
0.336 (1.00) |
0.0891 (1.00) |
0.253 (1.00) |
0.317 (1.00) |
0.795 (1.00) |
0.16 (1.00) |
0.115 (1.00) |
| ACSM2B | 38 (17%) | 190 |
0.658 (1.00) |
0.45 (1.00) |
0.792 (1.00) |
0.438 (1.00) |
0.371 (1.00) |
0.583 (1.00) |
0.296 (1.00) |
0.704 (1.00) |
| PPP6C | 18 (8%) | 210 |
0.558 (1.00) |
0.254 (1.00) |
0.0992 (1.00) |
0.79 (1.00) |
0.558 (1.00) |
0.653 (1.00) |
0.345 (1.00) |
0.113 (1.00) |
| LCE1B | 12 (5%) | 216 |
0.146 (1.00) |
0.605 (1.00) |
0.317 (1.00) |
0.858 (1.00) |
0.571 (1.00) |
0.795 (1.00) |
0.929 (1.00) |
0.91 (1.00) |
| MUC7 | 19 (8%) | 209 |
0.955 (1.00) |
0.487 (1.00) |
0.131 (1.00) |
0.713 (1.00) |
0.503 (1.00) |
0.0377 (1.00) |
0.087 (1.00) |
0.0497 (1.00) |
| OR51S1 | 27 (12%) | 201 |
0.316 (1.00) |
0.84 (1.00) |
0.884 (1.00) |
0.108 (1.00) |
0.383 (1.00) |
0.69 (1.00) |
0.63 (1.00) |
0.871 (1.00) |
| NAP1L2 | 23 (10%) | 205 |
0.7 (1.00) |
1 (1.00) |
0.802 (1.00) |
0.829 (1.00) |
0.598 (1.00) |
1 (1.00) |
0.922 (1.00) |
1 (1.00) |
| PRB2 | 31 (14%) | 197 |
0.509 (1.00) |
0.535 (1.00) |
0.733 (1.00) |
0.767 (1.00) |
0.0161 (1.00) |
0.0381 (1.00) |
0.196 (1.00) |
0.193 (1.00) |
| TAF1A | 13 (6%) | 215 |
0.676 (1.00) |
0.877 (1.00) |
0.546 (1.00) |
0.0838 (1.00) |
0.823 (1.00) |
0.388 (1.00) |
0.41 (1.00) |
0.914 (1.00) |
| HIST1H2AA | 10 (4%) | 218 |
0.363 (1.00) |
0.711 (1.00) |
0.652 (1.00) |
0.709 (1.00) |
0.399 (1.00) |
0.917 (1.00) |
0.315 (1.00) |
0.229 (1.00) |
| FRG2B | 16 (7%) | 212 |
0.898 (1.00) |
0.717 (1.00) |
0.975 (1.00) |
0.995 (1.00) |
0.25 (1.00) |
0.837 (1.00) |
0.603 (1.00) |
0.187 (1.00) |
| CDH9 | 33 (14%) | 195 |
0.839 (1.00) |
0.137 (1.00) |
0.216 (1.00) |
0.562 (1.00) |
0.817 (1.00) |
0.581 (1.00) |
0.00366 (1.00) |
0.419 (1.00) |
| PRAMEF11 | 21 (9%) | 207 |
0.773 (1.00) |
0.0631 (1.00) |
0.937 (1.00) |
0.952 (1.00) |
0.217 (1.00) |
0.497 (1.00) |
0.804 (1.00) |
0.631 (1.00) |
| HBG2 | 8 (4%) | 220 |
0.601 (1.00) |
0.421 (1.00) |
0.258 (1.00) |
0.344 (1.00) |
0.354 (1.00) |
0.894 (1.00) |
0.114 (1.00) |
0.206 (1.00) |
| DDX3X | 18 (8%) | 210 |
0.614 (1.00) |
0.951 (1.00) |
0.231 (1.00) |
0.176 (1.00) |
0.676 (1.00) |
0.949 (1.00) |
0.862 (1.00) |
0.208 (1.00) |
| PRB4 | 19 (8%) | 209 |
0.41 (1.00) |
0.564 (1.00) |
0.129 (1.00) |
0.174 (1.00) |
0.0299 (1.00) |
0.149 (1.00) |
0.361 (1.00) |
0.26 (1.00) |
| GRXCR1 | 18 (8%) | 210 |
0.867 (1.00) |
0.0729 (1.00) |
0.391 (1.00) |
0.955 (1.00) |
0.0392 (1.00) |
1 (1.00) |
0.636 (1.00) |
0.208 (1.00) |
| HHLA2 | 17 (7%) | 211 |
0.0519 (1.00) |
0.772 (1.00) |
0.456 (1.00) |
0.00441 (1.00) |
0.898 (1.00) |
0.0795 (1.00) |
0.015 (1.00) |
0.493 (1.00) |
| RBM11 | 13 (6%) | 215 |
0.242 (1.00) |
0.0394 (1.00) |
0.771 (1.00) |
0.881 (1.00) |
0.771 (1.00) |
0.0519 (1.00) |
0.213 (1.00) |
0.454 (1.00) |
| FUT9 | 22 (10%) | 206 |
0.418 (1.00) |
0.0258 (1.00) |
0.505 (1.00) |
0.861 (1.00) |
0.442 (1.00) |
0.254 (1.00) |
0.275 (1.00) |
0.678 (1.00) |
| TTN | 176 (77%) | 52 |
0.41 (1.00) |
0.0137 (1.00) |
0.495 (1.00) |
0.114 (1.00) |
0.198 (1.00) |
0.22 (1.00) |
0.119 (1.00) |
0.314 (1.00) |
| HBD | 10 (4%) | 218 |
0.3 (1.00) |
0.779 (1.00) |
0.832 (1.00) |
0.252 (1.00) |
0.0352 (1.00) |
0.166 (1.00) |
0.551 (1.00) |
0.891 (1.00) |
| KIAA1257 | 14 (6%) | 214 |
0.42 (1.00) |
0.941 (1.00) |
0.582 (1.00) |
0.747 (1.00) |
0.784 (1.00) |
0.765 (1.00) |
0.568 (1.00) |
0.515 (1.00) |
| USP17L2 | 19 (8%) | 209 |
0.229 (1.00) |
0.155 (1.00) |
0.167 (1.00) |
0.25 (1.00) |
0.24 (1.00) |
0.36 (1.00) |
0.279 (1.00) |
0.462 (1.00) |
| CADM2 | 23 (10%) | 205 |
0.729 (1.00) |
0.112 (1.00) |
0.169 (1.00) |
0.371 (1.00) |
0.675 (1.00) |
0.711 (1.00) |
0.276 (1.00) |
0.00591 (1.00) |
| GFRAL | 31 (14%) | 197 |
0.164 (1.00) |
0.212 (1.00) |
0.699 (1.00) |
0.741 (1.00) |
0.859 (1.00) |
0.874 (1.00) |
0.515 (1.00) |
0.96 (1.00) |
| OR4N2 | 22 (10%) | 206 |
0.299 (1.00) |
0.174 (1.00) |
0.614 (1.00) |
0.37 (1.00) |
0.0222 (1.00) |
0.23 (1.00) |
0.6 (1.00) |
0.185 (1.00) |
| UGT2B15 | 21 (9%) | 207 |
0.439 (1.00) |
0.38 (1.00) |
0.815 (1.00) |
0.74 (1.00) |
0.439 (1.00) |
0.873 (1.00) |
0.151 (1.00) |
0.345 (1.00) |
| UNC119B | 6 (3%) | 222 |
0.45 (1.00) |
0.45 (1.00) |
0.213 (1.00) |
0.92 (1.00) |
0.59 (1.00) |
0.551 (1.00) |
1 (1.00) |
0.462 (1.00) |
| RAPGEF5 | 12 (5%) | 216 |
1 (1.00) |
0.605 (1.00) |
0.627 (1.00) |
0.503 (1.00) |
0.491 (1.00) |
0.686 (1.00) |
0.238 (1.00) |
0.0624 (1.00) |
| C8A | 27 (12%) | 201 |
0.615 (1.00) |
0.0801 (1.00) |
0.256 (1.00) |
0.364 (1.00) |
0.112 (1.00) |
0.69 (1.00) |
0.34 (1.00) |
0.163 (1.00) |
| ANKRD20A4 | 5 (2%) | 223 |
0.27 (1.00) |
0.45 (1.00) |
0.32 (1.00) |
0.143 (1.00) |
0.23 (1.00) |
0.604 (1.00) |
0.616 (1.00) |
1 (1.00) |
| ELF5 | 6 (3%) | 222 |
1 (1.00) |
1 (1.00) |
0.934 (1.00) |
0.519 (1.00) |
0.59 (1.00) |
1 (1.00) |
0.204 (1.00) |
0.157 (1.00) |
| SPAG16 | 16 (7%) | 212 |
0.847 (1.00) |
0.849 (1.00) |
0.144 (1.00) |
0.306 (1.00) |
0.11 (1.00) |
0.123 (1.00) |
0.0725 (1.00) |
0.106 (1.00) |
| PHGDH | 9 (4%) | 219 |
0.48 (1.00) |
0.912 (1.00) |
1 (1.00) |
0.433 (1.00) |
0.763 (1.00) |
0.747 (1.00) |
0.766 (1.00) |
0.35 (1.00) |
| COPG2 | 9 (4%) | 219 |
0.321 (1.00) |
0.912 (1.00) |
0.271 (1.00) |
0.26 (1.00) |
0.692 (1.00) |
0.614 (1.00) |
0.907 (1.00) |
0.779 (1.00) |
| GML | 9 (4%) | 219 |
0.174 (1.00) |
0.378 (1.00) |
0.941 (1.00) |
0.429 (1.00) |
0.834 (1.00) |
0.902 (1.00) |
0.181 (1.00) |
0.779 (1.00) |
| TBC1D3B | 5 (2%) | 223 |
0.225 (1.00) |
0.848 (1.00) |
0.0591 (1.00) |
0.241 (1.00) |
0.861 (1.00) |
1 (1.00) |
0.853 (1.00) |
0.641 (1.00) |
| TFEC | 15 (7%) | 213 |
1 (1.00) |
0.592 (1.00) |
0.0568 (1.00) |
0.0742 (1.00) |
0.295 (1.00) |
1 (1.00) |
0.588 (1.00) |
0.728 (1.00) |
| TRAT1 | 13 (6%) | 215 |
1 (1.00) |
0.29 (1.00) |
0.731 (1.00) |
0.697 (1.00) |
0.317 (1.00) |
0.926 (1.00) |
0.312 (1.00) |
0.587 (1.00) |
| PRR23B | 15 (7%) | 213 |
0.392 (1.00) |
0.0371 (1.00) |
0.00685 (1.00) |
0.125 (1.00) |
0.531 (1.00) |
0.162 (1.00) |
0.09 (1.00) |
0.00109 (0.984) |
| C9ORF119 | 8 (4%) | 220 |
0.483 (1.00) |
0.598 (1.00) |
0.476 (1.00) |
0.56 (1.00) |
0.665 (1.00) |
0.387 (1.00) |
0.247 (1.00) |
0.304 (1.00) |
| LIN7A | 11 (5%) | 217 |
0.858 (1.00) |
0.179 (1.00) |
0.552 (1.00) |
0.644 (1.00) |
0.161 (1.00) |
0.605 (1.00) |
0.127 (1.00) |
0.81 (1.00) |
| PARM1 | 18 (8%) | 210 |
0.867 (1.00) |
1 (1.00) |
0.75 (1.00) |
0.142 (1.00) |
0.952 (1.00) |
0.851 (1.00) |
0.161 (1.00) |
0.39 (1.00) |
| CCK | 6 (3%) | 222 |
0.582 (1.00) |
0.658 (1.00) |
0.32 (1.00) |
0.0771 (1.00) |
0.447 (1.00) |
0.876 (1.00) |
0.576 (1.00) |
0.714 (1.00) |
| FIGLA | 3 (1%) | 225 |
0.629 (1.00) |
0.623 (1.00) |
0.514 (1.00) |
0.429 (1.00) |
0.472 (1.00) |
0.69 (1.00) |
||
| TCEB3C | 26 (11%) | 202 |
0.506 (1.00) |
0.309 (1.00) |
0.363 (1.00) |
0.557 (1.00) |
0.308 (1.00) |
0.0428 (1.00) |
0.666 (1.00) |
0.252 (1.00) |
| DEFB118 | 9 (4%) | 219 |
0.391 (1.00) |
0.216 (1.00) |
0.934 (1.00) |
0.284 (1.00) |
0.834 (1.00) |
0.614 (1.00) |
0.697 (1.00) |
0.779 (1.00) |
| VEGFC | 17 (7%) | 211 |
0.598 (1.00) |
0.12 (1.00) |
0.334 (1.00) |
0.0276 (1.00) |
0.197 (1.00) |
0.299 (1.00) |
0.0182 (1.00) |
0.148 (1.00) |
| MARCH11 | 11 (5%) | 217 |
1 (1.00) |
0.858 (1.00) |
0.374 (1.00) |
0.709 (1.00) |
0.161 (1.00) |
0.142 (1.00) |
1 (1.00) |
1 (1.00) |
| ZFP106 | 10 (4%) | 218 |
0.849 (1.00) |
0.779 (1.00) |
0.234 (1.00) |
0.257 (1.00) |
0.509 (1.00) |
0.917 (1.00) |
0.551 (1.00) |
0.447 (1.00) |
| PDE1A | 32 (14%) | 196 |
0.337 (1.00) |
0.913 (1.00) |
0.475 (1.00) |
0.406 (1.00) |
0.0361 (1.00) |
0.228 (1.00) |
0.523 (1.00) |
0.299 (1.00) |
| NUDT4 | 5 (2%) | 223 |
1 (1.00) |
0.372 (1.00) |
0.357 (1.00) |
0.151 (1.00) |
1 (1.00) |
0.837 (1.00) |
0.53 (1.00) |
0.498 (1.00) |
| FGF16 | 7 (3%) | 221 |
1 (1.00) |
0.797 (1.00) |
0.00469 (1.00) |
0.0157 (1.00) |
1 (1.00) |
0.148 (1.00) |
0.094 (1.00) |
0.524 (1.00) |
| OR4F6 | 15 (7%) | 213 |
0.943 (1.00) |
0.433 (1.00) |
0.433 (1.00) |
0.45 (1.00) |
0.04 (1.00) |
0.162 (1.00) |
0.13 (1.00) |
0.392 (1.00) |
| CD2 | 17 (7%) | 211 |
0.411 (1.00) |
0.41 (1.00) |
0.756 (1.00) |
0.54 (1.00) |
0.95 (1.00) |
0.758 (1.00) |
0.769 (1.00) |
0.703 (1.00) |
| EIF3D | 4 (2%) | 224 |
0.829 (1.00) |
0.836 (1.00) |
0.241 (1.00) |
0.419 (1.00) |
1 (1.00) |
0.361 (1.00) |
0.566 (1.00) |
0.429 (1.00) |
| MKX | 15 (7%) | 213 |
0.12 (1.00) |
0.21 (1.00) |
0.551 (1.00) |
0.977 (1.00) |
0.0795 (1.00) |
0.295 (1.00) |
0.314 (1.00) |
0.492 (1.00) |
| ARL16 | 7 (3%) | 221 |
0.18 (1.00) |
0.345 (1.00) |
0.138 (1.00) |
0.636 (1.00) |
0.391 (1.00) |
1 (1.00) |
1 (1.00) |
1 (1.00) |
| OR2L3 | 15 (7%) | 213 |
0.531 (1.00) |
0.0108 (1.00) |
0.744 (1.00) |
0.488 (1.00) |
0.892 (1.00) |
0.357 (1.00) |
0.889 (1.00) |
0.424 (1.00) |
| DEFB119 | 6 (3%) | 222 |
1 (1.00) |
0.77 (1.00) |
0.492 (1.00) |
0.88 (1.00) |
0.877 (1.00) |
0.876 (1.00) |
0.438 (1.00) |
1 (1.00) |
| KLHL4 | 21 (9%) | 207 |
0.807 (1.00) |
0.544 (1.00) |
0.788 (1.00) |
0.859 (1.00) |
0.208 (1.00) |
0.23 (1.00) |
0.841 (1.00) |
0.345 (1.00) |
| NR1H4 | 12 (5%) | 216 |
0.427 (1.00) |
0.246 (1.00) |
0.341 (1.00) |
0.375 (1.00) |
0.934 (1.00) |
0.58 (1.00) |
1 (1.00) |
0.371 (1.00) |
| IL32 | 9 (4%) | 219 |
0.391 (1.00) |
0.126 (1.00) |
0.688 (1.00) |
0.146 (1.00) |
0.528 (1.00) |
1 (1.00) |
0.629 (1.00) |
1 (1.00) |
| DGAT2L6 | 11 (5%) | 217 |
0.339 (1.00) |
0.536 (1.00) |
0.885 (1.00) |
0.12 (1.00) |
0.243 (1.00) |
0.605 (1.00) |
0.789 (1.00) |
0.81 (1.00) |
| OR8D4 | 11 (5%) | 217 |
0.585 (1.00) |
0.421 (1.00) |
0.0723 (1.00) |
0.0151 (1.00) |
0.207 (1.00) |
0.0707 (1.00) |
0.577 (1.00) |
0.667 (1.00) |
| GRXCR2 | 15 (7%) | 213 |
0.392 (1.00) |
0.945 (1.00) |
0.134 (1.00) |
0.653 (1.00) |
0.47 (1.00) |
0.468 (1.00) |
0.889 (1.00) |
0.791 (1.00) |
| OR5H2 | 15 (7%) | 213 |
0.707 (1.00) |
0.89 (1.00) |
0.432 (1.00) |
0.51 (1.00) |
0.892 (1.00) |
0.775 (1.00) |
0.488 (1.00) |
0.492 (1.00) |
| SIGLEC14 | 12 (5%) | 216 |
0.311 (1.00) |
0.246 (1.00) |
0.035 (1.00) |
0.445 (1.00) |
0.66 (1.00) |
0.795 (1.00) |
0.868 (1.00) |
0.91 (1.00) |
| ZNF479 | 24 (11%) | 204 |
0.657 (1.00) |
1 (1.00) |
0.739 (1.00) |
0.115 (1.00) |
0.533 (1.00) |
0.424 (1.00) |
0.074 (1.00) |
0.633 (1.00) |
| C2 | 12 (5%) | 216 |
0.0329 (1.00) |
0.288 (1.00) |
0.0549 (1.00) |
0.395 (1.00) |
0.0989 (1.00) |
0.58 (1.00) |
0.45 (1.00) |
0.415 (1.00) |
| GH2 | 10 (4%) | 218 |
0.0987 (1.00) |
0.601 (1.00) |
0.852 (1.00) |
0.88 (1.00) |
0.66 (1.00) |
0.585 (1.00) |
0.461 (1.00) |
0.573 (1.00) |
| GK2 | 29 (13%) | 199 |
0.771 (1.00) |
0.533 (1.00) |
0.357 (1.00) |
0.209 (1.00) |
0.701 (1.00) |
0.635 (1.00) |
0.15 (1.00) |
0.807 (1.00) |
| C2ORF40 | 7 (3%) | 221 |
0.236 (1.00) |
0.898 (1.00) |
0.941 (1.00) |
0.726 (1.00) |
0.892 (1.00) |
0.786 (1.00) |
0.381 (1.00) |
0.627 (1.00) |
| CXCR2 | 13 (6%) | 215 |
0.594 (1.00) |
0.336 (1.00) |
0.866 (1.00) |
0.954 (1.00) |
0.555 (1.00) |
0.558 (1.00) |
0.819 (1.00) |
0.914 (1.00) |
| RPTN | 39 (17%) | 189 |
0.315 (1.00) |
0.243 (1.00) |
0.329 (1.00) |
0.396 (1.00) |
0.0296 (1.00) |
0.329 (1.00) |
0.563 (1.00) |
0.452 (1.00) |
| PRIM2 | 13 (6%) | 215 |
0.366 (1.00) |
0.0625 (1.00) |
0.116 (1.00) |
0.456 (1.00) |
0.174 (1.00) |
0.0177 (1.00) |
0.503 (1.00) |
0.412 (1.00) |
| MUM1L1 | 26 (11%) | 202 |
0.629 (1.00) |
0.777 (1.00) |
0.799 (1.00) |
0.0988 (1.00) |
0.587 (1.00) |
0.155 (1.00) |
0.498 (1.00) |
0.587 (1.00) |
| TLL1 | 44 (19%) | 184 |
0.933 (1.00) |
0.0187 (1.00) |
0.67 (1.00) |
0.0508 (1.00) |
0.117 (1.00) |
0.103 (1.00) |
0.887 (1.00) |
0.456 (1.00) |
| PRC1 | 13 (6%) | 215 |
0.938 (1.00) |
0.448 (1.00) |
0.0597 (1.00) |
0.717 (1.00) |
0.32 (1.00) |
0.522 (1.00) |
0.312 (1.00) |
0.541 (1.00) |
| GLRB | 23 (10%) | 205 |
0.286 (1.00) |
0.464 (1.00) |
0.0598 (1.00) |
0.0346 (1.00) |
0.402 (1.00) |
0.266 (1.00) |
0.408 (1.00) |
0.5 (1.00) |
| AREG | 6 (3%) | 222 |
0.769 (1.00) |
0.581 (1.00) |
0.385 (1.00) |
0.287 (1.00) |
0.773 (1.00) |
0.216 (1.00) |
0.766 (1.00) |
0.462 (1.00) |
| SPINK13 | 8 (4%) | 220 |
0.14 (1.00) |
0.469 (1.00) |
0.893 (1.00) |
0.469 (1.00) |
0.44 (1.00) |
0.447 (1.00) |
0.22 (1.00) |
0.485 (1.00) |
| ACD | 9 (4%) | 219 |
0.289 (1.00) |
0.691 (1.00) |
0.47 (1.00) |
0.541 (1.00) |
0.394 (1.00) |
0.138 (1.00) |
0.0862 (1.00) |
0.0584 (1.00) |
| C2ORF39 | 9 (4%) | 219 |
0.391 (1.00) |
0.216 (1.00) |
0.866 (1.00) |
0.27 (1.00) |
0.0322 (1.00) |
0.018 (1.00) |
0.503 (1.00) |
0.889 (1.00) |
| RERG | 9 (4%) | 219 |
0.48 (1.00) |
0.579 (1.00) |
0.292 (1.00) |
0.228 (1.00) |
0.528 (1.00) |
0.437 (1.00) |
0.181 (1.00) |
0.688 (1.00) |
| TUBB8 | 13 (6%) | 215 |
0.635 (1.00) |
0.823 (1.00) |
0.212 (1.00) |
0.137 (1.00) |
0.425 (1.00) |
0.371 (1.00) |
0.471 (1.00) |
0.373 (1.00) |
| AGXT2 | 18 (8%) | 210 |
0.745 (1.00) |
1 (1.00) |
0.0959 (1.00) |
0.541 (1.00) |
0.746 (1.00) |
0.808 (1.00) |
0.738 (1.00) |
0.345 (1.00) |
| C9 | 16 (7%) | 212 |
0.949 (1.00) |
0.515 (1.00) |
0.874 (1.00) |
0.583 (1.00) |
0.723 (1.00) |
0.66 (1.00) |
0.896 (1.00) |
0.688 (1.00) |
| CX3CL1 | 4 (2%) | 224 |
0.14 (1.00) |
0.134 (1.00) |
1 (1.00) |
0.548 (1.00) |
0.122 (1.00) |
0.429 (1.00) |
||
| DEFB112 | 8 (4%) | 220 |
0.177 (1.00) |
0.421 (1.00) |
0.393 (1.00) |
0.616 (1.00) |
0.354 (1.00) |
0.447 (1.00) |
0.905 (1.00) |
0.421 (1.00) |
| FAM19A1 | 8 (4%) | 220 |
0.158 (1.00) |
0.379 (1.00) |
0.456 (1.00) |
0.117 (1.00) |
0.488 (1.00) |
1 (1.00) |
1 (1.00) |
0.876 (1.00) |
| LONRF2 | 16 (7%) | 212 |
1 (1.00) |
0.341 (1.00) |
0.944 (1.00) |
0.987 (1.00) |
0.948 (1.00) |
0.837 (1.00) |
0.43 (1.00) |
0.688 (1.00) |
| NAP1L4 | 9 (4%) | 219 |
0.0259 (1.00) |
0.0438 (1.00) |
0.035 (1.00) |
0.605 (1.00) |
0.636 (1.00) |
0.0606 (1.00) |
0.629 (1.00) |
1 (1.00) |
| OR5J2 | 14 (6%) | 214 |
0.574 (1.00) |
0.779 (1.00) |
0.319 (1.00) |
0.492 (1.00) |
1 (1.00) |
1 (1.00) |
0.0557 (1.00) |
0.37 (1.00) |
| POM121 | 14 (6%) | 214 |
0.474 (1.00) |
0.363 (1.00) |
0.299 (1.00) |
0.265 (1.00) |
0.694 (1.00) |
0.357 (1.00) |
0.883 (1.00) |
0.553 (1.00) |
| RBM22 | 7 (3%) | 221 |
0.437 (1.00) |
0.128 (1.00) |
0.342 (1.00) |
0.459 (1.00) |
1 (1.00) |
0.524 (1.00) |
||
| SLC10A2 | 20 (9%) | 208 |
0.426 (1.00) |
0.153 (1.00) |
0.748 (1.00) |
0.328 (1.00) |
0.16 (1.00) |
0.615 (1.00) |
0.478 (1.00) |
0.145 (1.00) |
| C4ORF22 | 11 (5%) | 217 |
0.634 (1.00) |
0.927 (1.00) |
0.621 (1.00) |
0.274 (1.00) |
0.861 (1.00) |
0.85 (1.00) |
0.138 (1.00) |
0.267 (1.00) |
| CLEC14A | 19 (8%) | 209 |
0.027 (1.00) |
0.347 (1.00) |
0.137 (1.00) |
0.478 (1.00) |
0.264 (1.00) |
0.604 (1.00) |
0.361 (1.00) |
1 (1.00) |
| GNAI2 | 4 (2%) | 224 |
1 (1.00) |
0.37 (1.00) |
0.696 (1.00) |
0.797 (1.00) |
0.834 (1.00) |
0.809 (1.00) |
0.219 (1.00) |
0.144 (1.00) |
| IGF2BP3 | 6 (3%) | 222 |
0.881 (1.00) |
0.883 (1.00) |
0.866 (1.00) |
0.659 (1.00) |
0.518 (1.00) |
1 (1.00) |
0.174 (1.00) |
0.714 (1.00) |
| RBM46 | 15 (7%) | 213 |
0.752 (1.00) |
0.172 (1.00) |
0.0872 (1.00) |
0.155 (1.00) |
0.944 (1.00) |
0.687 (1.00) |
0.458 (1.00) |
0.177 (1.00) |
| SERPINB4 | 30 (13%) | 198 |
0.752 (1.00) |
0.908 (1.00) |
0.395 (1.00) |
0.156 (1.00) |
0.218 (1.00) |
0.38 (1.00) |
0.635 (1.00) |
0.315 (1.00) |
| SORT1 | 10 (4%) | 218 |
0.92 (1.00) |
0.779 (1.00) |
1 (1.00) |
0.498 (1.00) |
0.253 (1.00) |
0.166 (1.00) |
1 (1.00) |
0.51 (1.00) |
P value = 2.22e-07 (Fisher's exact test), Q value = 2e-04
Table S1. Gene #2: 'BRAF MUTATION STATUS' versus Clinical Feature #1: 'CN_CNMF'
| nPatients | CLUS_1 | CLUS_2 | CLUS_3 |
|---|---|---|---|
| ALL | 76 | 63 | 89 |
| BRAF MUTATED | 24 | 49 | 44 |
| BRAF WILD-TYPE | 52 | 14 | 45 |
Figure S1. Get High-res Image Gene #2: 'BRAF MUTATION STATUS' versus Clinical Feature #1: 'CN_CNMF'
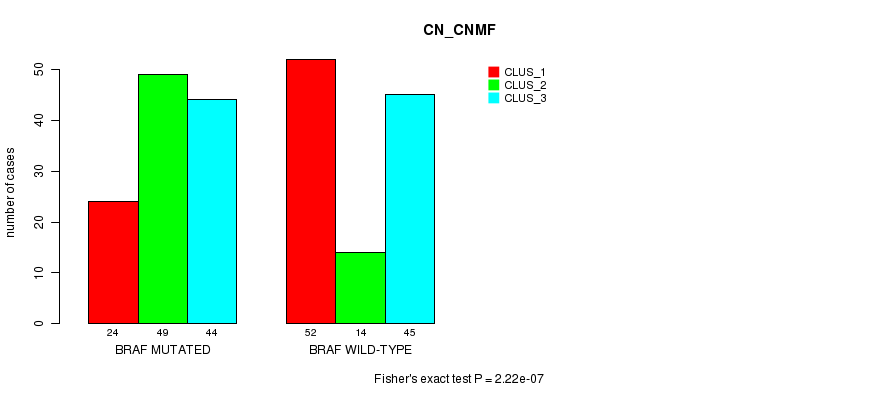
P value = 8.88e-05 (Fisher's exact test), Q value = 0.08
Table S2. Gene #2: 'BRAF MUTATION STATUS' versus Clinical Feature #6: 'MRNASEQ_CHIERARCHICAL'
| nPatients | CLUS_1 | CLUS_2 | CLUS_3 |
|---|---|---|---|
| ALL | 55 | 55 | 115 |
| BRAF MUTATED | 15 | 36 | 65 |
| BRAF WILD-TYPE | 40 | 19 | 50 |
Figure S2. Get High-res Image Gene #2: 'BRAF MUTATION STATUS' versus Clinical Feature #6: 'MRNASEQ_CHIERARCHICAL'
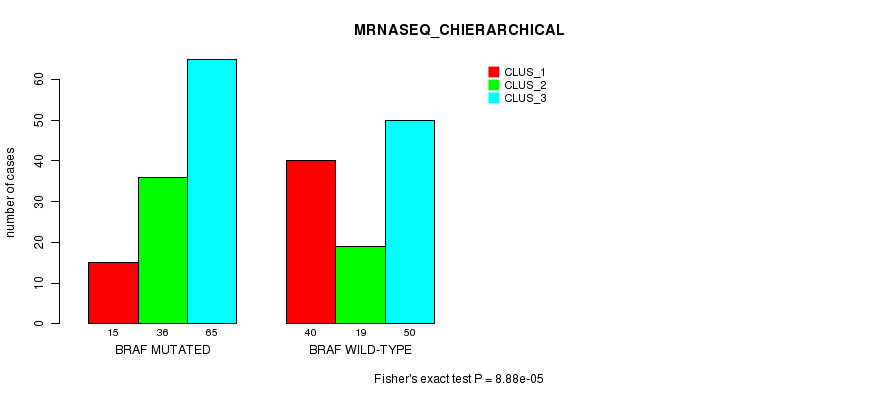
-
Mutation data file = SKCM-All_Metastatic.mutsig.cluster.txt
-
Molecular subtypes file = SKCM-All_Metastatic.transferedmergedcluster.txt
-
Number of patients = 228
-
Number of significantly mutated genes = 114
-
Number of Molecular subtypes = 8
-
Exclude genes that fewer than K tumors have mutations, K = 3
For binary or multi-class clinical features (nominal or ordinal), two-tailed Fisher's exact tests (Fisher 1922) were used to estimate the P values using the 'fisher.test' function in R
For multi-class clinical features (nominal or ordinal), Chi-square tests (Greenwood and Nikulin 1996) were used to estimate the P values using the 'chisq.test' function in R
For multiple hypothesis correction, Q value is the False Discovery Rate (FDR) analogue of the P value (Benjamini and Hochberg 1995), defined as the minimum FDR at which the test may be called significant. We used the 'Benjamini and Hochberg' method of 'p.adjust' function in R to convert P values into Q values.
This is an experimental feature. The full results of the analysis summarized in this report can be downloaded from the TCGA Data Coordination Center.